Visualizar Tese - Instituto de Biociências - Unesp
Visualizar Tese - Instituto de Biociências - Unesp Visualizar Tese - Instituto de Biociências - Unesp
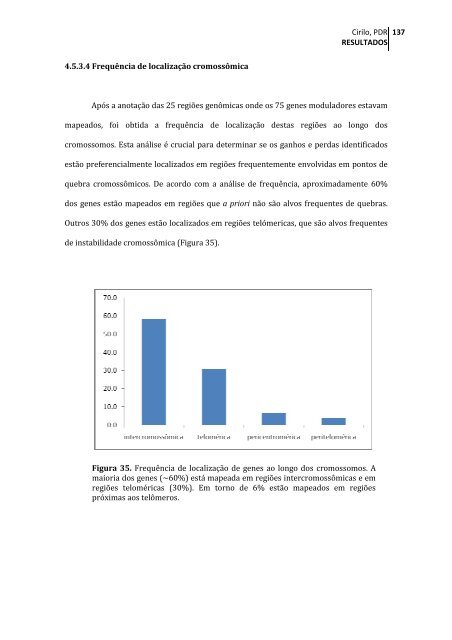
Cirilo, PDRRESULTADOS1374.5.3.4 Frequência de localização cromossômicaApós a anotação das 25 regiões genômicas onde os 75 genes moduladores estavammapeados, foi obtida a frequência de localização destas regiões ao longo doscromossomos. Esta análise é crucial para determinar se os ganhos e perdas identificadosestão preferencialmente localizados em regiões frequentemente envolvidas em pontos dequebra cromossômicos. De acordo com a análise de frequência, aproximadamente 60%dos genes estão mapeados em regiões que a priori não são alvos frequentes de quebras.Outros 30% dos genes estão localizados em regiões telómericas, que são alvos frequentesde instabilidade cromossômica (Figura 35).Figura 35. Frequência de localização de genes ao longo dos cromossomos. Amaioria dos genes (~60%) está mapeada em regiões intercromossômicas e emregiões teloméricas (30%). Em torno de 6% estão mapeados em regiõespróximas aos telômeros.
Cirilo, PDRRESULTADOS1384.5.3.5 Meta-análise com dados públicos – GEOOs 75 genes moduladores foram comparados ao banco de dados GEO (GeneExpression Omnibus - http://www.ncbi.nlm.nih.gov/geo/) onde estão depositados osresultados de estudos de expressão gênica em larga escala, incluindo cinco estudos emLeiomiomas Uterinos. Esta análise permitiu identificar genes que já foram associados comLU e também a descrição de novos transcritos. Estes estudos estão armazenados sob osseguintes códigos: GSE764 (Quade et al., 2004), GSE593 (Hoffman et al., 2004), GSE2152(Vanharanta et al., 2005), GSE13319 (Crabtree et al., 2009) e GSE12814 (Hodge et al.,2009), respectivamente (Tabela 13).Todos os 75 genes foram identificados em pelo menos três dos cinco estudosprévios. Estes genes apresentaram diferentes padrões de expressão, onde 52 deles (69%)apresentaram o mesmo padrão de expressão em pelo menos um estudo depositado noGEO.
- Page 110 and 111: Cirilo, PDRRESULTADOS87Figura 19. R
- Page 112 and 113: Cirilo, PDRRESULTADOS894.3.1 Análi
- Page 114 and 115: Cirilo, PDRRESULTADOS91Figura 22. A
- Page 116 and 117: Cirilo, PDRRESULTADOS93Entre os cas
- Page 118 and 119: Cirilo, PDRRESULTADOS95Figura 23. A
- Page 120 and 121: Cirilo, PDRRESULTADOS97Tabela 8. Ge
- Page 122 and 123: Cirilo, PDRRESULTADOS99HAPLN1 HAPLN
- Page 124 and 125: Cirilo, PDRRESULTADOS101beta 4MYO10
- Page 126 and 127: Cirilo, PDRRESULTADOS103DIO1 DIO1 d
- Page 128 and 129: Cirilo, PDRRESULTADOS105inhibits CD
- Page 130 and 131: Cirilo, PDRRESULTADOS107CENPK CENPK
- Page 132 and 133: Cirilo, PDRRESULTADOS109pareamento
- Page 134 and 135: Cirilo, PDRRESULTADOS111JUB, ↓MAG
- Page 136 and 137: Cirilo, PDRRESULTADOS113Figura 25.
- Page 138 and 139: Cirilo, PDRRESULTADOS115Figura 27.
- Page 140 and 141: Cirilo, PDRRESULTADOS117Figura 29.
- Page 142 and 143: Cirilo, PDRRESULTADOS1194.5.1 CGH a
- Page 144 and 145: Cirilo, PDRRESULTADOS121Figura 32.
- Page 146 and 147: Cirilo, PDRRESULTADOS123Tabela 10.
- Page 148 and 149: Cirilo, PDRRESULTADOS125
- Page 150 and 151: Cirilo, PDRRESULTADOS1274.5.3.1 Pre
- Page 152 and 153: Cirilo, PDRRESULTADOS129PKP3 - -PRE
- Page 154 and 155: Cirilo, PDRRESULTADOS131Tabela 12.
- Page 156 and 157: Cirilo, PDRRESULTADOS133Perda (1) N
- Page 158 and 159: ABCirilo, PDRRESULTADOS135Figura 33
- Page 162 and 163: Cirilo, PDRRESULTADOS139Tabela 13.
- Page 164 and 165: Cirilo, PDRRESULTADOS1414.5.3.6 An
- Page 166 and 167: Cirilo, PDRRESULTADOS143Tabela 15.
- Page 168 and 169: Cirilo, PDRRESULTADOS145ativação
- Page 170 and 171: ACirilo, PDRRESULTADOS147BFigura 36
- Page 172 and 173: Cirilo, PDRRESULTADOS149Figura 38.
- Page 174 and 175: Cirilo, PDRDISCUSSÃO1515. Discuss
- Page 177 and 178: Cirilo, PDRDISCUSSÃO154informaçõ
- Page 179 and 180: Cirilo, PDRDISCUSSÃO156descritos g
- Page 181 and 182: Cirilo, PDRDISCUSSÃO158uma proteí
- Page 183 and 184: Cirilo, PDRDISCUSSÃO160celulares e
- Page 185 and 186: Cirilo, PDRDISCUSSÃO162apresentado
- Page 187 and 188: Cirilo, PDRDISCUSSÃO164q14). Porta
- Page 189 and 190: Cirilo, PDRDISCUSSÃO166Desde 1991,
- Page 191 and 192: Cirilo, PDRDISCUSSÃO168núcleo das
- Page 193 and 194: Cirilo, PDRDISCUSSÃO170sobre LHFPL
- Page 195 and 196: Cirilo, PDRDISCUSSÃO172outras cate
- Page 197 and 198: Cirilo, PDRDISCUSSÃO174Entre as ou
- Page 199 and 200: Cirilo, PDRDISCUSSÃO176regiões de
- Page 201 and 202: Cirilo, PDRDISCUSSÃO178da RNA Pol
- Page 203 and 204: Cirilo, PDRDISCUSSÃO180proliferati
- Page 205 and 206: Cirilo, PDRDISCUSSÃO182Entre os 20
- Page 207 and 208: Cirilo, PDRDISCUSSÃO184propôs um
- Page 209 and 210: Cirilo, PDRDISCUSSÃO186analisados
Cirilo, PDRRESULTADOS1374.5.3.4 Frequência <strong>de</strong> localização cromossômicaApós a anotação das 25 regiões genômicas on<strong>de</strong> os 75 genes moduladores estavammapeados, foi obtida a frequência <strong>de</strong> localização <strong>de</strong>stas regiões ao longo doscromossomos. Esta análise é crucial para <strong>de</strong>terminar se os ganhos e perdas i<strong>de</strong>ntificadosestão preferencialmente localizados em regiões frequentemente envolvidas em pontos <strong>de</strong>quebra cromossômicos. De acordo com a análise <strong>de</strong> frequência, aproximadamente 60%dos genes estão mapeados em regiões que a priori não são alvos frequentes <strong>de</strong> quebras.Outros 30% dos genes estão localizados em regiões telómericas, que são alvos frequentes<strong>de</strong> instabilida<strong>de</strong> cromossômica (Figura 35).Figura 35. Frequência <strong>de</strong> localização <strong>de</strong> genes ao longo dos cromossomos. Amaioria dos genes (~60%) está mapeada em regiões intercromossômicas e emregiões teloméricas (30%). Em torno <strong>de</strong> 6% estão mapeados em regiõespróximas aos telômeros.