14.duplicazione DNA - Docente.unicas.it
14.duplicazione DNA - Docente.unicas.it
14.duplicazione DNA - Docente.unicas.it
You also want an ePaper? Increase the reach of your titles
YUMPU automatically turns print PDFs into web optimized ePapers that Google loves.
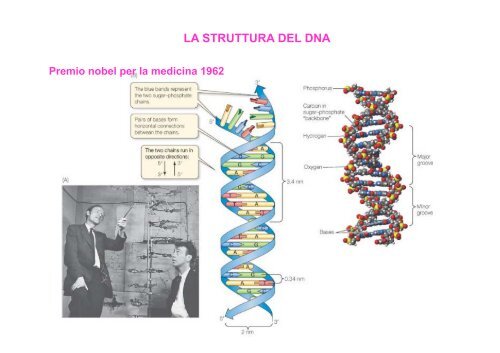
Premio nobel per la medicina 1962<br />
LA STRUTTURA DEL <strong>DNA</strong>
STRUTTURA <strong>DNA</strong> (acido deossiribonucleico)<br />
BASI AZOTATE<br />
adenina (A)<br />
c<strong>it</strong>osina (C)<br />
guanina (G)<br />
timina (T).<br />
Adenina e guanina sono composti eterociclici chiamati purine, mentre c<strong>it</strong>osina e timina<br />
sono anelli pirimidinici.<br />
Doppia elica antiparallela<br />
Una sequenza di <strong>DNA</strong> è defin<strong>it</strong>a senso<br />
se la sua sequenza è la stessa del<br />
relativo mRNA. La sequenza posta sul<br />
filamento opposto è invece detta<br />
antisenso. Dal momento che le RNA<br />
polimerasi lavorano producendo una<br />
copia complementare, il filamento<br />
necessario per la trascrizione è<br />
l'antisenso.<br />
gruppo fosfato<br />
deossiribosio (zucchero pentoso)<br />
base azotata<br />
Si forma un legame covalente tra il gruppo fosfato di un nucleotide e lo zucchero del nucleotide<br />
precedente
Gruppo fosfato<br />
zucchero<br />
BASE AZOTATA<br />
I NUCLEOTIDI<br />
Il <strong>DNA</strong> è un polimero<br />
I suoi monomeri<br />
sono i NUCLEOTIDI<br />
I nucleotidi sono formati<br />
Gruppo fosfato<br />
zucchero deossiribosio<br />
base azotata
PURINE<br />
PIRIMIDINE<br />
Le basi azotate
La complementarietà<br />
una purina si appaia con una<br />
pirimidina<br />
L’adenina si appaia con la<br />
timina (2 legami H)<br />
La guanina si appaia con la<br />
c<strong>it</strong>osina (3 legami H)
Le 2 catene di<br />
nucleotidi si<br />
avvolgono l’una<br />
sull’altra a spirale<br />
per questo la<br />
molecola di <strong>DNA</strong><br />
viene chiamata<br />
la DOPPIA ELICA<br />
•la molecola può venire duplicata facilmente<br />
•il <strong>DNA</strong> viene utilizzato dai viventi come un codice<br />
per registrare e trasmettere informazioni
Funzioni del <strong>DNA</strong><br />
• Materiale ered<strong>it</strong>ario: viene duplicato e<br />
trasmesso alle cellule figlie<br />
• Programma della cellula: contiene le<br />
informazioni per la sintesi di tutte le proteine<br />
dell’organismo<br />
• Ogni tratto di <strong>DNA</strong> che porta l’informazione per<br />
la sintesi di una proteina→GENE<br />
• Nel <strong>DNA</strong> delle cellule della specie umana ci<br />
sono circa 30.000 geni, in quello di un batterio,<br />
poche migliaia
REPLICAZIONE SEMICONSERVATIVA<br />
È il processo attraverso il quale da una molecola madre si formano due molecole figlie ciascuna formata da<br />
un’elica vecchia e un’elica nuova. La duplicazione del Dna avviene nella fase S (sintesi) del ciclo cellulare.<br />
L’enzima che permette questo processo si chiama <strong>DNA</strong> polimerasi. Una volta che è avvenuta la<br />
duplicazione del <strong>DNA</strong> la cellula deve dividersi.<br />
Nei batteri il <strong>DNA</strong> si duplica a partire da una<br />
forcella di replicazione in modo bidirezionale<br />
fino a quando tutta la molecola si è duplicata
Meselson e Stahl fecero crescere dei batteri in un terreno di coltura ricco dell'isotopo pesante 15 N. Questi microorganismi<br />
metabolizzarono l' 15 N che quindi venne ad essere introdotto in molte molecole biologiche; tra queste molecole bisogna<br />
ricordare le basi azotate del <strong>DNA</strong>.<br />
In questo modo il <strong>DNA</strong> presente nei batteri era un "<strong>DNA</strong> pesante", poiché inglobava atomi di azoto più pesanti della norma.<br />
Alcuni batteri furono poi prelevati, lisati e, con opportune tecniche di laboratorio, venne estratto il loro <strong>DNA</strong>.<br />
Quest'ultimo venne aggiunto ad una provetta contenente una soluzione concentrata di Cloruro di Cesio (CsCl 6M).<br />
La provetta fu poi centrifugata. In queste condizioni nella provetta si forma un gradiente di dens<strong>it</strong>à dal momento che il CsCl<br />
tende a concentrarsi verso il fondo della stessa.<br />
•Una volta che si è formato il gradiente di dens<strong>it</strong>à, il <strong>DNA</strong> migra per fermarsi<br />
nella regione della soluzione che ha dens<strong>it</strong>à uguale alla sua.<br />
Il <strong>DNA</strong> può essere messo in evidenza in segu<strong>it</strong>o all'introduzione di particolari<br />
sostanze che si legano ad esso e divengono visibili se illuminate da luce<br />
ultravioletta.<br />
Ciò che si vide sperimentalmente fu una banda verso il fondo della provetta.<br />
•A questo punto alcuni batteri furono trasfer<strong>it</strong>i dal primo terreno di coltura in un<br />
nuovo terreno "standard", in cui cioè era presente 14N anziché 15N. I<br />
microorganismi metabolizzarono l'azoto includendolo nelle basi azotate dei<br />
nucleotidi che andranno a formare (tra le altre cose) le nuove eliche di <strong>DNA</strong>.<br />
•Alcuni batteri furono prelevati dal terreno "standard", furono lisati e venne<br />
estratto il <strong>DNA</strong>.<br />
•In segu<strong>it</strong>o ad una centrifugazione in gradiente di dens<strong>it</strong>à si ottenne un'unica<br />
banda posta in posizione superiore rispetto a quella del caso precedente: il<br />
<strong>DNA</strong> era quindi più leggero.<br />
•Trascorso il tempo necessario per la successiva replicazione del <strong>DNA</strong> venne<br />
ripetuta la suddetta procedura.<br />
In questo caso si ottennero due bande: la prima in posizione nettamente<br />
superiore a quelle ottenute nei casi precedenti, la seconda nella stessa<br />
posizione di quella dell'esperimento precedente.<br />
A questo punto possiamo identificare:<br />
un <strong>DNA</strong> "pesante". In cui per forza erano presenti due filamenti 15N.<br />
un <strong>DNA</strong> "medio". In cui per forza era presente un filamento 15N e un filamento<br />
14N.<br />
un <strong>DNA</strong> "leggero". In cui per forza erano presenti due filamenti 14N.
…….l'unico modello in grado di spiegare i "pesi" delle varie molecole di <strong>DNA</strong> era quello della replicazione<br />
semiconservativa
Ingredienti della replicazione del <strong>DNA</strong>
REPLICAZIONE <strong>DNA</strong> PROCARIOTICO<br />
1 ORIGINE DI REPLICAZIONE<br />
PROCESSO BIDIREZIONALE<br />
CI SONO 2 FORCELLE DI REPLICAZIONE CHE SI MUOVONO IN VERSI OPPOSTI E CHE AL TERMINE DEL<br />
PROCESSO SI “INCONTRANO<br />
L'origine di replicazione di Escherichia coli, nota come oriC, consiste di<br />
ripetizioni di una sequenza di nucleotidi.<br />
La DnaA è una proteina deputata al riconoscimento e al legame di tali<br />
ripetizioni.determina la denaturazione della regione ricca in A/T e crea<br />
quindi regioni a singolo filamento<br />
La <strong>DNA</strong> ELICASI separa i filamenti dall’origine in direzione 5’-3’<br />
Ci sono proteine che impediscono che le eliche si richiudano.<br />
La <strong>DNA</strong> POLMERASI e’ l’enzima che catalizza la polimerizzazione dei<br />
desossiribonucleotidi. catalizza il legame covalente tra il gruppo fosfato<br />
di un nucleotide e lo zucchero del nucleotide precedente
<strong>DNA</strong> polimerasi I meccanismo di riparazione<br />
<strong>DNA</strong> polimerasi II meccanismo di riparazione<br />
<strong>DNA</strong> polimerasi III sintesi dei filamenti di <strong>DNA</strong>. Estende la catena aggiungendo un<br />
nucleotide per volta all’estremo 3’-OH<br />
Le <strong>DNA</strong> polimerasi<br />
batteriche hanno<br />
un’attiv<strong>it</strong>à esonucleol<strong>it</strong>ica<br />
3’-5’ (direzione opposta a<br />
quella di sintesi)
La sintesi del <strong>DNA</strong> inizia in un punto in cui la molecola viene<br />
preventivamente srotolata chiamato origine. Si forma così un'ansa di<br />
replicazione alla cui estrem<strong>it</strong>à troviamo le "forcelle di replicazione" e la<br />
sintesi può proseguire in due direzioni. Nel <strong>DNA</strong> batterico circolare, le<br />
forcelle si incontrano in un punto della circonferenza opposto<br />
all'origine.
Poiché le eliche sono antiparallele, ne consegue che un'elica, chiamata catena<br />
leader, o stampo, viene letta e copiata nella direzione di avanzamento della<br />
forcella e procede in modo continuo e veloce (un unico innesco a RNA). L'altra<br />
elica dovrà essere sintetizzata con r<strong>it</strong>ardo e in modo discontinuo dovendo<br />
attendere lo srotolamento dell'elica veloce. Okazaki, biologo giapponese, scoprì<br />
che la catena discontinua viene sintetizzata, con frammenti, in direzione opposta<br />
all'avanzamento della forcella.<br />
E' da tenere presente che ogni frammento di Okazaki termina con un'estrem<strong>it</strong>à<br />
3'OH libera<br />
Ha una struttura asimmetrica:<br />
– leading strand sintetizzato con continu<strong>it</strong>à<br />
– Lagging strand sintetizzato con discontinu<strong>it</strong>à
•Le <strong>DNA</strong> polimerasi non possono sintetizzare catene di <strong>DNA</strong> senza un primer, un piccolo segmento<br />
di acido nucleico con un gruppo ossidrilico libero in posizione 3’-OH.<br />
•Le <strong>DNA</strong> polimerasi sono capaci di leggere nucleotidi solo nella direzione 5’-3’<br />
Durante la replicazione del materiale genetico, il primer è cost<strong>it</strong>u<strong>it</strong>o da RNA.<br />
Una RNA polimerasi <strong>DNA</strong>-dipendente, detta primasi, sintetizza un piccolo tratto di RNA<br />
complementare allo stampo molecolare, utilizzato come primer dalla <strong>DNA</strong> polimerasi .<br />
Una volta iniziata la sintesi di <strong>DNA</strong>, il primer di RNA viene diger<strong>it</strong>o da enzimi con attiv<strong>it</strong>à 5’ →3’<br />
esonucleasica.<br />
La reazione di polimerizzazione richiede i quattro precursori attivati, dATP, dGTP, dCTP e dTTP ed<br />
avviene direttamente sulla catena di <strong>DNA</strong> stampo.<br />
Nel filamento guida la <strong>DNA</strong> polimerasi può attaccare i nucleotidi in direzione 5’-3’ a partire<br />
dall’innesco<br />
Nel filamento lento la sintesi procede sempre in direzione 5’-3’ ma in direzione opposta a quella<br />
della forcella di replicazione
LE PROTEINE “INIZIATRICI” SI LEGANO CON INTERAZIONI<br />
SEQUENZE SPECIFICHE ALLE ORIGINI DI REPLICAZIONI<br />
RICCHE IN A-T
Il legame dei dNTP allo stampo avviene mediante i legami idrogeno, ma anche la forma delle basi e<br />
controlli sterici nel s<strong>it</strong>o attivo della <strong>DNA</strong>-polimerasi, concorrono al corretto appaiamento delle basi<br />
La frequenza di errore viene ridotta anche grazie ad accurati meccanismi enzimatici.<br />
Tutte le <strong>DNA</strong> polimerasi possiedono un’attiv<strong>it</strong>à esonucleasica 3’→5’ che consente di rimuovere un<br />
nucleotide appena inser<strong>it</strong>o Tale attiv<strong>it</strong>à di “proof reading” (lettura delle bozze) è altamente specifica<br />
per gli appaiamenti sbagliati e aggiunge un ulteriore fattore di accuratezza che riduce la frequenza di<br />
errore totale.<br />
La <strong>DNA</strong> polimerasi è in grado di rimuovere gli inneschi a RNA e di riempire i gap con il <strong>DNA</strong>. I<br />
frammenti vengono poi un<strong>it</strong>i dalla <strong>DNA</strong> ligasi<br />
Dalla parte opposta rispetto a Ori C il cromososma di E. Coli contiene un paio di sequenze di<br />
terminazione TER<br />
Una proteina si lega a queste sequenze e vengono bloccate le forcelle di replicazione<br />
La <strong>DNA</strong> ligasi lega tutti e quattro i filamenti di <strong>DNA</strong> creando due molecole circolari a doppio<br />
filamento concatenate.<br />
Le topoisomerasi sono enzimi che provocano delle rotture temporanee nei filamenti di <strong>DNA</strong> e poi li<br />
riuniscono dopo la formazione di due molecole circolari distinte
L'elicasi è un enzima che agisce rompendo i legami idrogeno instaurati tra le basi complementari.<br />
Inoltre questo enzima agisce in coppia con la <strong>DNA</strong>-girasi che separa i 2 filamenti di <strong>DNA</strong>.<br />
Le topoisomerasi determinano un aumento o una diminuzione del grado di superavvolgimento. Possono<br />
operare tagli a singolo o doppio filamento. Tali enzimi svolgono un ruolo fondamentale<br />
nell'impacchettamento e nella replicazione del <strong>DNA</strong>.<br />
Primasi:All'inizio della replicazione del <strong>DNA</strong>, le primasi legano le elicasi a formare un complesso<br />
chiamato primosoma. Attivate proprio dalle elicasi, le primasi sintetizzano una breve molecola di RNA<br />
(detta appunto primer), complementare alla molecola di <strong>DNA</strong> adiacente. Il primer viene utilizzato poi<br />
come punto di partenza per le <strong>DNA</strong> polimerasi.<br />
Ligasi: lega due frammenti di <strong>DNA</strong> che hanno sub<strong>it</strong>o una rottura a doppio filamento (ad esempio nei<br />
processi di riparazione del <strong>DNA</strong>).<br />
Può anche legare una rottura a singolo filamento, come ad esempio accade durante il processo di<br />
replicazione del <strong>DNA</strong>, nel quale la <strong>DNA</strong> ligasi agisce sul filamento che ha la direzione 3'->5', sintetizzato a<br />
frammenti .<br />
Questo enzima catalizza infatti la formazione di legami covalenti fosfodiesterici tra nucleotidi di <strong>DNA</strong><br />
adiacenti (lega l'estrem<strong>it</strong>à 3' del nuovo tratto di <strong>DNA</strong> con l'estrem<strong>it</strong>à 5' del tratto precedentemente<br />
sintetizzato).<br />
ATP + (deossiribonucleotide)n + (deossiribonucleotide)m = AMP + difosfato +<br />
(deossiribonucleotide)n+m
Il processo di replicazione del <strong>DNA</strong> nei procarioti e negli eucarioti è molto simile,<br />
ma nelle cellule eucariote la quant<strong>it</strong>à di <strong>DNA</strong> è maggiore ed è organizzato in<br />
strutture lineari<br />
Esistono 2 tipi di cromatina:<br />
1)EUCROMATINA (+dispersa e si colora debolmente) e<br />
2)ETEROCROMATINA (+ condensata si colora + intensamente).
I Genomi degli Eucarioti:<br />
Eucromatina ed Eterocromatina<br />
Eucromatina: regioni cromosomiche non condensate, attivamente trascr<strong>it</strong>te e ad<br />
alta dens<strong>it</strong>à genica (fibre 30 nm).<br />
Eterocromatina: (facoltativa o cost<strong>it</strong>utiva): cromatina mediamente o altamente<br />
condensata e generalmente non trascr<strong>it</strong>ta, ad alta percentuale di sequenze<br />
ripetute e contenuto di geni relativamente basso. Comprende regioni telomeriche<br />
e centromeriche.<br />
In una tipica cellula di mammifero il contenuto di eterocromatina è pari a circa il 10%. in<br />
Drosophila melanogaster cost<strong>it</strong>uisce il 34% del genoma totale.<br />
24
I Genomi degli Eucarioti: contenuto in <strong>DNA</strong><br />
Si osserva che il contenuto totale di <strong>DNA</strong> negli eucarioti e quindi la<br />
dimensione del genoma è correlata alla compless<strong>it</strong>à dell’organismo (ad<br />
es., il genoma umano è più grande di quello degli insetti che è a sua volta<br />
più grande di quello funghi).<br />
Esistono però diverse eccezioni: es. il genoma di X. laevis è grande quanto<br />
quello dei mammiferi; altri anfibi hanno un genoma circa 50 volte più<br />
grande del genoma umano; tra le piante, il genoma di Zea Mais èpiù<br />
grande di quello umano.<br />
In genere, per un dato raggruppamento tassonomico, la dimensione del<br />
genoma è approssimativamente proporzionale alla compless<strong>it</strong>à<br />
dell’organismo<br />
25
Paradosso del valore C<br />
La mancanza di correlazione tra la compless<strong>it</strong>à genetica/morfologica di<br />
un organismo e le dimensioni del suo genoma è defin<strong>it</strong>a<br />
Paradosso del valore C.<br />
Il Paradosso del valore C è spiegato considerando:<br />
• le dimensioni dei geni discontinui<br />
(numero - grandezza introni)<br />
• La quant<strong>it</strong>à di <strong>DNA</strong> ripet<strong>it</strong>ivo, che rappresenta il componente più<br />
abbondante della porzione di <strong>DNA</strong> non codificante dei genomi<br />
eucariotici
REPLICAZIONE <strong>DNA</strong> EUCARIOTICO<br />
PIU’ ORIGIN DI REPLICAZIONE ARS (sequenza replicante autonoma ricca in A-T))<br />
Ogni origine di replicazione prende il nome di replicone, da cui il processo si avvia in maniera<br />
bidirezionale<br />
Riduzione del tempo di replicazione<br />
LE FORCELLE REPLICATIVE ENTRANO IN CONTATTO TRA LORO<br />
5 <strong>DNA</strong> POLIMERASI:<br />
αβδε: agiscono nel nucleo<br />
γ: agisce nei m<strong>it</strong>ocondri<br />
α,δ: replicazione <strong>DNA</strong> cromosomico<br />
β, ε: riparazione danni al <strong>DNA</strong><br />
Sintesi di istoni che formano ottameri e si associano al <strong>DNA</strong> nella<br />
forcella replicativa
Il telomero è la regione terminale del cromosoma, composta di <strong>DNA</strong> altamente ripetuto, che non<br />
codifica per alcun prodotto proteico.<br />
Ha un ruolo determinante nell'ev<strong>it</strong>are la perd<strong>it</strong>a di informazioni durante la duplicazione dei<br />
cromosomi.<br />
Le sequenze telomeriche variano da organismo in organismo.<br />
Il <strong>DNA</strong> telomerico è sintetizzato dalle telomerasi, <strong>DNA</strong> polimerasi RNA-dipendenti altamente<br />
specializzate che introducono centinaia di ripetizioni nucleotidiche alle estrem<strong>it</strong>à dei cromosomi.<br />
E’ una classe di retrotrascr<strong>it</strong>tasi specializzate, presenti in numerosi organismi (tra cui l'uomo), ma<br />
non in tutti (e soprattutto non in tutte le fasi dello sviluppo). Utilizza frammenti di RNA come<br />
stampo per l'elongazione dei telomeri.<br />
E’ capace di allungare l'estrem<strong>it</strong>à 3'-OH del filamento stampo della catena tardiva.<br />
Contiene un s<strong>it</strong>o catal<strong>it</strong>ico che polimerizza i desossiribonucleotidi complementari ad un RNA<br />
stampo, che essa stessa contiene.<br />
In particolare, nell'uomo le telomerasi sono attive solo nelle cellule della linea germinale: ciò<br />
significa che, ad ogni replicazione, i telomeri umani si accorciano di un certo numero di paia di<br />
basi.<br />
La <strong>DNA</strong> polimerasi non è in grado di replicare il cromosoma fino alla sua terminazione; se non ci<br />
fossero i telomeri, che quindi vengono accorciati ad ogni replicazione, la replicazione del <strong>DNA</strong><br />
comporterebbe in ogni occasione una significativa perd<strong>it</strong>a di informazione genetica.<br />
I telomeri si accorciano a causa del meccanismo di replicazione del filamento lagging del <strong>DNA</strong>.<br />
l’ultimo primer di RNA viene tagliato ma non sost<strong>it</strong>u<strong>it</strong>o con il <strong>DNA</strong><br />
Questo genera un continuo processo di accorciamento di queste regioni
SEQUENZA DI RNA COMPLEMENTARE ALLE<br />
SEQUENZE RIPETUTE NEI TELOMERI
LA TELOMERASI SI LEGA ALL’ESTREMITA’ 3’ A SINGOLO FILAMENTO DEL CROMOSOMA
L’ALLUNGAMENTO DEL 3’ DEL TELOMERO CREA LO SPAZIO PER LA<br />
FORMAZIONE DI UN NUOVO FRAMMENTO DI OKAZAKI
Esistono teorie che associano il continuo accorciarsi dei telomeri con la senescenza delle<br />
cellule della linea somatica e con la prevenzione del cancro. Questo perché i telomeri<br />
agirebbero come una sorta di orologio biologico, legato cioè ad un numero massimo di<br />
m<strong>it</strong>osi (e di replicazioni del <strong>DNA</strong>), al termine del quale la cellula sarebbe troppo vecchia per<br />
essere mantenuta in v<strong>it</strong>a e prenderebbe la via dell‘apoptosi.<br />
La telomerasi è espressa dalle cellule embrionali ma non dalle cellule somatiche dell’organismo<br />
Adulto<br />
Le uniche eccezioni sono cost<strong>it</strong>u<strong>it</strong>e dalle cellule germinali e da quelle attivamente proliferanti<br />
(cellule staminali, strati basali ep<strong>it</strong>eliali<br />
il mantenimento della lunghezza dei telomeri è un segno distintivo di molti tipi di cancro nei<br />
mammiferi. Nell'uomo, ad esempio, numerosi tumori sono in grado di aumentare l'attiv<strong>it</strong>à<br />
della telomerasi, ottenendo una capac<strong>it</strong>à di replicazione pressoché infin<strong>it</strong>a. Altri tipi di<br />
carcinoma, invece, sono in grado di avviare pathway alternativi di allungamento dei telomeri
Tutte le cellule possono dividersi un numero<br />
defin<strong>it</strong>o di volte: CPD (Divisioni Cellulari<br />
Permesse)
Una volta raggiunto il CPD la cellula<br />
entra nella “senescenza replicativa”,<br />
cioè l’incapac<strong>it</strong>à di<br />
proliferare ulteriormente<br />
Interviene il processo di<br />
APOPTOSI,<br />
che porta<br />
alla morte della cellula
La lunghezza dei telomeri determina il numero di divisioni cellulari permesse. Il CPD dipende<br />
dal tipo di cellula e dal tessuto di cui essa fa parte. Quando i telomeri raggiungono una<br />
lunghezza “cr<strong>it</strong>ica” la cellula entra nella senescenza replicativa perchè viene emesso un<br />
segnale che impedisce alla cellula di dividersi ancora.<br />
Se vengono a mancare i sistemi di controllo della p53 o della p16/Rb, la cellula supera la fase di<br />
senescenza e può riattivare la telomerasi diventando immortale
Nelle cellule cancerose:<br />
L’attiv<strong>it</strong>à della telomerasi si<br />
incrementa dell’80-90%<br />
I telomeri sono più corti del normale
Per mutazione genetica si intende ogni modificazione stabile ed ered<strong>it</strong>abile nella<br />
sequenza nucleotidica di un genoma o più generalmente di materiale genetico (sia<br />
<strong>DNA</strong> che RNA) dovuta o al caso, ma non alla ricombinazione genetica. Una<br />
mutazione modifica quindi il genotipo di un individuo e può eventualmente<br />
modificarne il fenotipo a seconda delle sue caratteristiche e delle interazioni con<br />
l'ambiente.
Le mutazioni spontanee sono mutazioni provocate da fattori chimici endogeni e da errori nei processi che si attuano sul<br />
materiale genetico; la definizione di mutazione spontanea è di mutazione che avviene in assenza di agenti mutageni noti. Non<br />
sono molto frequenti, ma sono comunque inev<strong>it</strong>abili vista la intrinseca imperfezione di ogni meccanismo molecolare.<br />
Gli errori possono essere dovuti a:<br />
Reazioni che trasformano una base azotata in una diversa<br />
Errori nei processi di replicazione, della ricombinazione e della riparazione del <strong>DNA</strong>. Ad esempio può essere dovuta alla <strong>DNA</strong><br />
polimerasi che aggiunge nucleotidi non corretti; ciò può generare una trasversione se c'è lo scambio di una purina con una<br />
pirimidina o viceversa; una transizione se c'è lo scambio di una purina con un'altra purina oppure di una pirimidina con un'altra<br />
pirimidina.<br />
Danni ossidativi<br />
Dovuti alla formazione spontanea nella cellula di specie con atomi di ossigeno molto reattive, in grado di attaccare il <strong>DNA</strong> e<br />
causare danni al singolo o al doppio filamento e danneggiamento delle basi azotate.<br />
Le mutazioni indotte sono invece prodotte dall'azione di particolari agenti fisici o chimici detti appunto agenti mutageni. È detto<br />
mutagenesi il processo che determina una mutazione indotta e mutagenizzato l'organismo in cui è stata prodotta.<br />
Si distinguono i danni per mutazioni indotte in:<br />
Sost<strong>it</strong>uzione delle basi con molecole con struttura analoga a quelle comunemente presenti nel <strong>DNA</strong> ma che formano appaiamenti<br />
diversi e quindi errati.<br />
Aggiunta di gruppi sost<strong>it</strong>uenti alle basi azotate: anche in questo caso generando molecole con capac<strong>it</strong>à di appaiamento non<br />
corrette.<br />
Danneggiamento delle basi azotate<br />
Inserzione o delezioni di basi.<br />
I mutageni fisici sono soprattutto radiazioni ionizzanti (raggi X, raggi gamma) e non ionizzanti (raggi UV);<br />
Gli agenti chimici sono molto numerosi e appartengono a diverse classi di composti. Oltre che per la natura i mutageni<br />
differiscono anche per spettro mutazionale, ovvero per il tipo (o i tipi) di mutazione che possono provocare.<br />
Una importante differenza tra mutageni fisici e chimici è che i primi agiscono indipendentemente dall'organismo; i mutageni<br />
chimici invece possono avere effetti diversi in funzione del sistema biologico. Mentre una radiazione, infatti, colpisce direttamente<br />
il materiale genetico, un composto chimico può interagire con altre molecole (enzimi, metabol<strong>it</strong>i, specie reattive...) presenti nella<br />
cellula che ne possono variare le caratteristiche.
MUTAZIONI (classificazione in base ai meccanismi di<br />
generazione):<br />
•Inserzioni<br />
•Delezioni<br />
•Sost<strong>it</strong>uzione di basi
inserzioni di basi:<br />
•Riguardano uno o pochi nucleotidi<br />
•Conseguenze gravi se nel <strong>DNA</strong> codificante<br />
•Espansioni di triplette ripetute (CGG)
• Delezioni di basi<br />
•Riguardano uno o pochi nucleotidi<br />
•Conseguenze gravi se nel <strong>DNA</strong> codificante<br />
•Piu’ comuni a livello di sequenze ripetute in tandem<br />
(VNTR) per crossing-over ineguale
• Sost<strong>it</strong>uzioni di basi:<br />
•Transizioni = Sost<strong>it</strong>uzioni di purina (A o G) con<br />
un’altra purina (G o A) o di una pirimidina (T o C) con<br />
un’altra pirimidina (C o T)<br />
•Transversioni = Sost<strong>it</strong>uzioni di purina (A o G) con<br />
una pirimidina (T o C) o viceversa
• MUTAZIONI (classificazione in base alle conseguenze<br />
funzionali)<br />
•Sost<strong>it</strong>uzione che riguarda regioni potenzialmente<br />
rilevanti (esoni, regioni regolatrici espressione, s<strong>it</strong>i di<br />
splicing e poliadenilazione, regioni conservate in specie<br />
diverse)<br />
•Sost<strong>it</strong>uzione che riguarda sequenze senza un<br />
significato funzionale
• MUTAZIONI (classificazione in base alle conseguenze<br />
funzionali)<br />
Sost<strong>it</strong>uzioni in regioni potenzialmente rilevanti da un punto<br />
di vista funzionale<br />
•Sost<strong>it</strong>uzione sinonima o silente: non determina un<br />
cambio di aminoacido<br />
•Sost<strong>it</strong>uzione non sinonima: determina un codone<br />
specificante un aminoacido differente rispetto a<br />
quello originario.<br />
Puo’ essere:<br />
Conservativa (aminoacido simile da un punto di vista<br />
biochimico)<br />
Non conservativa (aminoacido diverso da un punto di<br />
vista biochimico)<br />
• Mutazione non senso: sost<strong>it</strong>uzione di un codone che<br />
specifica un aminoacido con un codone di fine sintesi
CODICE GENETICO<br />
U U U Phe U C U Ser U A U Tyr U G U Cys<br />
U U C Phe U C C Ser U A C Tyr U G C Cys<br />
U U A Leu U C A Ser U A A STOP U G A STOP<br />
U U G Leu U C G Ser U A G STOP U G G Trp<br />
C U U Leu C C U Pro C A U His C G U Arg<br />
C U C Leu C C C Pro C A C His C G C Arg<br />
C U A Leu C C A Pro C A A Gln C G A Arg<br />
C U G Leu C C G Pro C A G Gln C G G Arg<br />
A U U Ile A C U Thr A A U Asn A G U Ser<br />
A U C Ile A C C Thr A A C Asn A G C Ser<br />
A U A Ile A C A Thr A A A Lys A G A Arg<br />
A U G Met A C G Thr A A G Lys A G G Arg<br />
G U U Val G C U Ala G A U Asp G G U Gly<br />
G U C Val G C C Ala G A C Asp G G C Gly<br />
G U A Val G C A Ala G A A Glu G G A Gly<br />
G U G Val G C G Ala G A G Glu G G G Gly
MUTAZIONI FRAMESHIFT<br />
Le mutazioni frameshift (dall'inglese, spostamento dell'ordine di lettura) sono dette anche<br />
mutazioni da scivolamento. Sono causate dall'aggiunta (inserzione) o l'eliminazione<br />
(delezione) di uno o pochi nucleotidi. Nel caso di inserzione o delezione di nucleotidi in<br />
numero non multiplo di tre, viene alterato l'ordine di lettura di tutti i codoni successivi<br />
nell'ordine a quello inser<strong>it</strong>o o deleto. Scoperte da Crick e Brenner studiando il codice<br />
genetico, si tratta di mutazioni quasi sempre dannose.
Gli effetti possono essere notevolmente diversi a seconda del tipo di mutazione e della posizione<br />
in cui questa si verifica.<br />
Una mutazione può non portare a nessuna conseguenza e questo quando interessa <strong>DNA</strong> che non<br />
codifica (o meglio sembra non codificare) per nessun prodotto genico<br />
Se la mutazione va invece ad alterare le sequenze codificanti, ovvero i geni, si ha una variazione<br />
nel tipo o nella quant<strong>it</strong>à del corrispettivo prodotto genico, che può essere una proteina o RNA<br />
funzionale (rRNA, tRNA, snRNA ecc.). Parliamo in questo caso di mutazione biochimica.<br />
se la mutazione biochimica porta a una variazione visibile del fenotipo si parla di mutazione<br />
morfologica.<br />
Inoltre distinguiamo, sempre in relazione agli effetti, in:<br />
mutazione pos<strong>it</strong>iva: porta un vantaggio evolutivo<br />
mutazione neutra: non risulta in un depotenziamento della capac<strong>it</strong>à riproduttiva dell’individuo;<br />
mutazione semiletale: rende più difficoltosa la perpetuazione riproduttiva dell’individuo (il tipico<br />
esempio sono le malattie genetiche che debil<strong>it</strong>ano in qualche modo l’individuo, rendendolo meno<br />
capace di riprodursi, senza però impedirglielo totalmente)<br />
mutazione subletale: non permette all’individuo di raggiungere l’età riproduttiva;<br />
mutazione letale: porta alla morte dell'individuo in fase embrionale o fetale.
FOTODIMERIZZAZONE<br />
Il dimero di timina si forma tra due residui di timina posti sullo stesso lato della doppia elica<br />
del <strong>DNA</strong>, per azione della luce ultravioletta.<br />
Il dimero causa una distorsione nella doppia elica del <strong>DNA</strong> che ne impedisce la replicazione<br />
e l’espressione.<br />
Questo danno viene riparato a opera di diversi enzimi (nell’ E. coli si tratta di tre attiv<strong>it</strong>à<br />
enzimatiche) che riconoscono la distorsione, tagliano la porzione danneggiata e<br />
ricostruiscono le parti mancanti.<br />
Il dimero di timina può anche essere tagliato fotochimicamente, in quanto quasi tutte le<br />
cellule contengono un enzima fotoattivatore che si lega al dimero di timina e, assorbendo un<br />
fotone (fotoriattivazione), taglia il dimero nelle sue basi originali, favorendo il r<strong>it</strong>orno alla<br />
condizione iniziale.<br />
FOTOLIASI<br />
SISTEMI DI RIPARAZIONE<br />
La fotoliasi ha alta affin<strong>it</strong>à per queste strutture chimiche, alle quali si lega reversibilmente e<br />
le ripara. Questo enzima funziona come un meccanismo di riparazione del <strong>DNA</strong> quando la<br />
luce di lunghezza d'onda compresa fra 320 e 370 nm lo colpisce attivandolo. La reazione<br />
enzimatica prevede la rottura del dimero e la ricost<strong>it</strong>uzione della struttura corretta delle basi<br />
(fotoriattivazione).
Deaminazione della c<strong>it</strong>osina<br />
La deaminazione ossidativa spontanea della<br />
c<strong>it</strong>osina determina la formazione di uracile, con<br />
rilascio di ione ammonio.<br />
Verrà quindi inser<strong>it</strong>o un uracile al posto della<br />
corretta c<strong>it</strong>osina; l'appaiamento errato può<br />
essere riconosciuto e riparato da particolari<br />
sistemi di riparazione del <strong>DNA</strong>: in particolare<br />
specifiche glicosidasi riconoscono questo<br />
nucleotide che non è comune nel <strong>DNA</strong> e lo<br />
sost<strong>it</strong>uiscono con la c<strong>it</strong>osina.<br />
Deaminazione della 5-metilc<strong>it</strong>osina<br />
La deaminazione di questa base provoca la<br />
formazione di timina, un nucleotide<br />
normalmente presente nel <strong>DNA</strong>. Alcune<br />
gilcolidasi sono in grado di riconoscere gli<br />
appaiamenti errarti che derivano da questa<br />
deaminazione (T-G) e sost<strong>it</strong>uire alla timina la<br />
c<strong>it</strong>osina. La 5-metilc<strong>it</strong>osina è presente<br />
soprattutto nei procarioti, formata in segu<strong>it</strong>o a<br />
metilazione di una c<strong>it</strong>osina tram<strong>it</strong>e una metil<br />
transferasi. La formazione di questa base<br />
modificata è correlata a processi di<br />
silenziamento genico. Spesso la 5-metilc<strong>it</strong>osina<br />
è presenti nei s<strong>it</strong>i CpG:
Meccanismi per escissione di basi (BER):<br />
•Ripara il danno che coinvolge un solo nucleotide<br />
•<strong>DNA</strong> glicosilasi riconosce e rimuove la base alterata<br />
•L’endonucleasi rimuove lo zucchero e il gruppo fosforico<br />
•Una <strong>DNA</strong> POLIMERASI riempie il buco<br />
•Una <strong>DNA</strong> ligasi unisce i filamenti<br />
Meccanismi per escissione di nucleotidi (NER):<br />
•Ripara il danno di frammenti da 2 a 20 nucleotidi<br />
•Utilizza differenti enzimi (nulceasi, elicasi, <strong>DNA</strong><br />
polimerasi, <strong>DNA</strong> ligasi) rispetto al BER e rimuove più<br />
basi<br />
Mismatch Repair (MMR)<br />
corregge errori di replicazione e di ricombinazione<br />
genetica che determinano la formazione di nucleotidi<br />
male appaiati in segu<strong>it</strong>o alla replicazione del <strong>DNA</strong>.
Meccanismi di risposta cellulare al danno del <strong>DNA</strong><br />
•La cellula reagisce ad un danno del <strong>DNA</strong> mettendo in opera<br />
una serie di strategie per confinare e lim<strong>it</strong>are il danno.<br />
•In particolare si ha l’arresto del ciclo cellulare fino alla<br />
riparazione del danno. Questo meccanismo avviene grazie ad<br />
una serie di proteine<br />
•La prima è chiamata ATM, un sensore intracellulare in grado<br />
di avvertire il danno del <strong>DNA</strong>.<br />
•ATM, rilascia un segnale ad una seconda proteina P53 che<br />
viene fosforilata e stabilizzata. P53 è un fattore trascrizionale<br />
che è stato denominato il guardiano del genoma.<br />
•P53 quando è attivata da ATM attiva a sua volta altre<br />
proteine (p21) che bloccano il ciclo cellulare fino alla<br />
riparazione del danno.
Meccanismi di risposta cellulare al danno del <strong>DNA</strong><br />
•Se il danno del <strong>DNA</strong> non viene riparato P53 attiva altre<br />
proteine che determinano apoptosi (morte cellulare<br />
programmata).<br />
•Difetti del gene TP53 sul cromosoma 17 che codifica per P53<br />
causano una sindrome denominata Sindrome di Li-Fraunemi.<br />
•Nelle famiglie con Sindrome di Li-Fraunemi si osservano<br />
numerosi casi di differenti tumori ad esordio prima dei 50<br />
anni di v<strong>it</strong>a
Mutazioni che non vengono<br />
riconosciute come tali e quindi non<br />
vengono corrette<br />
MALATTIE GENETICHE<br />
MALATTIE MOLECOLARI<br />
MALATTIE METABOLICHE<br />
Una malattia genetica è una patologia la cui causa è ins<strong>it</strong>a nel genoma dell'individuo; può essere dovuta<br />
alla presenza di uno o più alleli che producono polipeptidi con struttura e funzional<strong>it</strong>à anomala o alla mal<br />
regolazione nell'espressione di geni "normali".<br />
Una malattia molecolare è causata da un'anomalia o da una carenza di una particolare molecola<br />
Una malattia metabolica è un’alterazione più o meno grave delle reazioni chimiche endocellulari e dei loro<br />
sistemi di controllo<br />
protoncogeni<br />
Proteine che controllano la<br />
replicazione e il differenziamento<br />
cellulare<br />
mutazione<br />
oncogeni cancro<br />
Perd<strong>it</strong>a del controllo dell’attiv<strong>it</strong>à<br />
proliferativa<br />
Gli oncogeni e i geni oncosoppressori sono geni che in condizioni normali sono coinvolti nella regolazione della<br />
cresc<strong>it</strong>a delle cellule: gli oncogeni stimolano la proliferazione cellulare, mentre gli oncosoppressori la inibiscono.
VIRUS ONCOGENI:<br />
Presenza nel loro genoma di un oncogene derivato dal trasferimento di una parte di<br />
un protooncogene proveniente dal genoma di una cellula eucariotica parass<strong>it</strong>ata.<br />
Dopo l’infezione, la proteina codificata dall’oncogene del genoma virale, inizia a<br />
svolgere la sua funzione, portando ad un aumento della riproduzione cellulare, che<br />
non viene più controllata