Quantitative Analyse von Protein-Massenspektren
Quantitative Analyse von Protein-Massenspektren Quantitative Analyse von Protein-Massenspektren
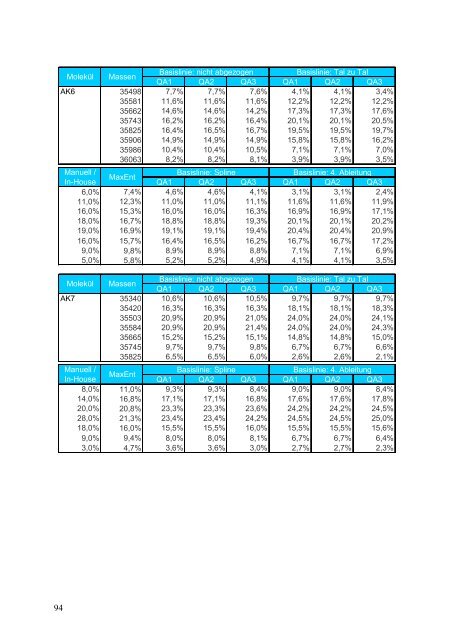
Molekül Massen Basislinie: nicht abgezogen QA1 QA2 QA3 Basislinie: Tal zu Tal QA1 QA2 QA3 AK6 35498 7,7% 7,7% 7,6% 4,1% 4,1% 3,4% 35581 11,6% 11,6% 11,6% 12,2% 12,2% 12,2% 35662 14,6% 14,6% 14,2% 17,3% 17,3% 17,6% 35743 16,2% 16,2% 16,4% 20,1% 20,1% 20,5% 35825 16,4% 16,5% 16,7% 19,5% 19,5% 19,7% 35906 14,9% 14,9% 14,9% 15,8% 15,8% 16,2% 35986 10,4% 10,4% 10,5% 7,1% 7,1% 7,0% 36063 8,2% 8,2% 8,1% 3,9% 3,9% 3,5% 94 Manuell / In-House MaxEnt QA1 Basislinie: Spline QA2 QA3 Basislinie: 4. Ableitung QA1 QA2 QA3 6,0% 7,4% 4,6% 4,6% 4,1% 3,1% 3,1% 2,4% 11,0% 12,3% 11,0% 11,0% 11,1% 11,6% 11,6% 11,9% 16,0% 15,3% 16,0% 16,0% 16,3% 16,9% 16,9% 17,1% 18,0% 16,7% 18,8% 18,8% 19,3% 20,1% 20,1% 20,2% 19,0% 16,9% 19,1% 19,1% 19,4% 20,4% 20,4% 20,9% 16,0% 15,7% 16,4% 16,5% 16,2% 16,7% 16,7% 17,2% 9,0% 9,8% 8,9% 8,9% 8,8% 7,1% 7,1% 6,9% 5,0% 5,8% 5,2% 5,2% 4,9% 4,1% 4,1% 3,5% Molekül Massen Basislinie: nicht abgezogen QA1 QA2 QA3 Basislinie: Tal zu Tal QA1 QA2 QA3 AK7 35340 10,6% 10,6% 10,5% 9,7% 9,7% 9,7% 35420 16,3% 16,3% 16,3% 18,1% 18,1% 18,3% 35503 20,9% 20,9% 21,0% 24,0% 24,0% 24,1% 35584 20,9% 20,9% 21,4% 24,0% 24,0% 24,3% 35665 15,2% 15,2% 15,1% 14,8% 14,8% 15,0% 35745 9,7% 9,7% 9,8% 6,7% 6,7% 6,6% 35825 6,5% 6,5% 6,0% 2,6% 2,6% 2,1% Manuell / In-House MaxEnt QA1 Basislinie: Spline QA2 QA3 Basislinie: 4. Ableitung QA1 QA2 QA3 8,0% 11,0% 9,3% 9,3% 8,4% 9,0% 9,0% 8,4% 14,0% 16,8% 17,1% 17,1% 16,8% 17,6% 17,6% 17,8% 20,0% 20,8% 23,3% 23,3% 23,6% 24,2% 24,2% 24,5% 28,0% 21,3% 23,4% 23,4% 24,2% 24,5% 24,5% 25,0% 18,0% 16,0% 15,5% 15,5% 16,0% 15,5% 15,5% 15,6% 9,0% 9,4% 8,0% 8,0% 8,1% 6,7% 6,7% 6,4% 3,0% 4,7% 3,6% 3,6% 3,0% 2,7% 2,7% 2,3%
Molekül Massen Basislinie: nicht abgezogen QA1 QA2 QA3 Basislinie: Tal zu Tal QA1 QA2 QA3 AK8 35342 13,2% 13,2% 12,9% 12,3% 12,3% 12,2% 35422 19,2% 19,2% 19,4% 22,4% 22,4% 22,4% 35504 23,1% 23,1% 23,3% 27,3% 27,3% 27,8% 35586 21,9% 21,9% 22,1% 24,7% 24,7% 25,2% 35668 13,8% 13,8% 13,8% 10,6% 10,6% 10,4% 35747 8,7% 8,7% 8,5% 2,7% 2,7% 2,0% Manuell / In-House MaxEnt QA1 Basislinie: Spline QA2 QA3 Basislinie: 4. Ableitung QA1 QA2 QA3 13,0% 13,5% 11,6% 11,6% 10,8% 13,2% 13,2% 13,0% 21,0% 20,3% 20,5% 20,5% 21,1% 19,2% 19,2% 19,4% 26,0% 23,7% 26,3% 26,3% 26,5% 23,1% 23,1% 23,3% 24,0% 23,1% 24,5% 24,5% 24,8% 21,9% 21,9% 22,2% 12,0% 14,0% 12,4% 12,4% 12,4% 13,8% 13,8% 13,7% 4,0% 5,5% 4,7% 4,7% 4,4% 8,7% 8,7% 8,4% Molekül Massen Basislinie: nicht abgezogen QA1 QA2 QA3 Basislinie: Tal zu Tal QA1 QA2 QA3 AK9 35341 14,1% 14,1% 14,0% 14,4% 14,4% 14,1% 35422 20,3% 20,3% 20,3% 24,3% 24,3% 24,5% 35504 22,3% 22,3% 22,4% 25,2% 25,2% 25,7% 35585 22,8% 22,8% 22,9% 26,3% 26,3% 27,1% 35667 11,7% 11,7% 11,6% 6,5% 6,5% 6,2% 35744 8,9% 8,9% 8,8% 3,3% 3,3% 2,5% Manuell / In-House MaxEnt QA1 Basislinie: Spline QA2 QA3 Basislinie: 4. Ableitung QA1 QA2 QA3 16,0% 14,8% 12,9% 12,9% 12,3% 13,6% 13,6% 13,4% 24,0% 21,9% 22,0% 22,0% 21,1% 23,8% 23,8% 24,3% 23,0% 23,1% 25,0% 25,0% 25,3% 25,8% 25,8% 26,1% 24,0% 24,5% 25,7% 25,7% 27,1% 27,3% 27,3% 27,9% 9,0% 10,5% 9,4% 9,4% 9,5% 6,2% 6,2% 5,9% 4,0% 5,2% 5,2% 5,2% 4,7% 3,3% 3,3% 2,5% Molekül Massen Basislinie: nicht abgezogen QA1 QA2 QA3 Basislinie: Tal zu Tal QA1 QA2 QA3 AK10 50601 47,0% 49,8% 49,9% 62,0% 64,3% 69,4% * 50763 23,6% 24,2% 25,6% 21,8% 22,7% 23,5% 50927 14,0% 12,9% 11,2% 7,8% 6,6% 4,1% 49152 15,4% 13,1% 13,4% 8,4% 6,5% 3,0% Manuell / In-House MaxEnt QA1 Basislinie: Spline QA2 QA3 Basislinie: 4. Ableitung QA1 QA2 QA3 69,0% 69,0% 54,4% 56,9% 59,9% 57,6% 59,4% 74,7% 25,6% 28,0% 23,1% 24,1% 24,8% 21,7% 22,7% 21,4% 3,4% 2,9% 10,3% 9,6% 7,7% 10,5% 9,6% 2,9% 2,0% 0,1% 12,2% 9,4% 7,6% 10,2% 8,3% 0,9% 95
- Seite 44 und 45: Liste werden durch eine kubische Sp
- Seite 46 und 47: Dieser Mechanismus funktioniert nur
- Seite 48 und 49: tionen zu berechnen, multipliziert
- Seite 50 und 51: Der Algorithmus für die Berechnung
- Seite 52 und 53: 3.5. Simulation der Peakverbreiteru
- Seite 54 und 55: die Peakbreite nicht konstant ist.
- Seite 56 und 57: Um die Parameter der Basisfunktione
- Seite 58 und 59: 58 ⎛ df1 ⎜ ⎜ dx1 J ( x) = ⎜
- Seite 60 und 61: 60 2 R =1 − SSE SSM (3.6.2.1) SSE
- Seite 62 und 63: Um diese Probleme zu umgehen, werde
- Seite 64 und 65: Möglichkeit a) konnte nach einem B
- Seite 66 und 67: Ionisierungen beschränkt. Dies kan
- Seite 68 und 69: DLL ist die Methode DLLEXPORT int M
- Seite 70 und 71: statten gehen und zweitens nicht in
- Seite 72 und 73: ten Hüllkurve gezogen. Basierend a
- Seite 74 und 75: um vertreten sind, muss man Abstric
- Seite 76 und 77: Die Auswertung der Spektren findet
- Seite 78 und 79: Bei der manuellen Quantifizierung g
- Seite 80 und 81: Ein ähnliches Bild bietet sich, we
- Seite 82 und 83: Die Daten aus Anhang A sind in Tabe
- Seite 84 und 85: Ebenso wie bei der Simulation präs
- Seite 86 und 87: Im Hinblick auf die technische Umse
- Seite 88 und 89: 88 Molekül Massen Referenz Manuell
- Seite 90 und 91: 90 Basislinie: Tal zu Tal Basislini
- Seite 92 und 93: B. Quantifizierungsergebnisse empir
- Seite 96 und 97: Molekül Massen Basislinie: nicht a
- Seite 98 und 99: Auf die Abbildung der dritten Seite
- Seite 100 und 101: 100
- Seite 102 und 103: Haver05 Prof. Tom O’Haver, Introd
Molekül Massen<br />
Basislinie: nicht abgezogen<br />
QA1 QA2 QA3<br />
Basislinie: Tal zu Tal<br />
QA1 QA2 QA3<br />
AK6 35498 7,7% 7,7% 7,6% 4,1% 4,1% 3,4%<br />
35581 11,6% 11,6% 11,6% 12,2% 12,2% 12,2%<br />
35662 14,6% 14,6% 14,2% 17,3% 17,3% 17,6%<br />
35743 16,2% 16,2% 16,4% 20,1% 20,1% 20,5%<br />
35825 16,4% 16,5% 16,7% 19,5% 19,5% 19,7%<br />
35906 14,9% 14,9% 14,9% 15,8% 15,8% 16,2%<br />
35986 10,4% 10,4% 10,5% 7,1% 7,1% 7,0%<br />
36063 8,2% 8,2% 8,1% 3,9% 3,9% 3,5%<br />
94<br />
Manuell /<br />
In-House<br />
MaxEnt<br />
QA1<br />
Basislinie: Spline<br />
QA2 QA3<br />
Basislinie: 4. Ableitung<br />
QA1 QA2 QA3<br />
6,0% 7,4% 4,6% 4,6% 4,1% 3,1% 3,1% 2,4%<br />
11,0% 12,3% 11,0% 11,0% 11,1% 11,6% 11,6% 11,9%<br />
16,0% 15,3% 16,0% 16,0% 16,3% 16,9% 16,9% 17,1%<br />
18,0% 16,7% 18,8% 18,8% 19,3% 20,1% 20,1% 20,2%<br />
19,0% 16,9% 19,1% 19,1% 19,4% 20,4% 20,4% 20,9%<br />
16,0% 15,7% 16,4% 16,5% 16,2% 16,7% 16,7% 17,2%<br />
9,0% 9,8% 8,9% 8,9% 8,8% 7,1% 7,1% 6,9%<br />
5,0% 5,8% 5,2% 5,2% 4,9% 4,1% 4,1% 3,5%<br />
Molekül Massen<br />
Basislinie: nicht abgezogen<br />
QA1 QA2 QA3<br />
Basislinie: Tal zu Tal<br />
QA1 QA2 QA3<br />
AK7 35340 10,6% 10,6% 10,5% 9,7% 9,7% 9,7%<br />
35420 16,3% 16,3% 16,3% 18,1% 18,1% 18,3%<br />
35503 20,9% 20,9% 21,0% 24,0% 24,0% 24,1%<br />
35584 20,9% 20,9% 21,4% 24,0% 24,0% 24,3%<br />
35665 15,2% 15,2% 15,1% 14,8% 14,8% 15,0%<br />
35745 9,7% 9,7% 9,8% 6,7% 6,7% 6,6%<br />
35825 6,5% 6,5% 6,0% 2,6% 2,6% 2,1%<br />
Manuell /<br />
In-House<br />
MaxEnt<br />
QA1<br />
Basislinie: Spline<br />
QA2 QA3<br />
Basislinie: 4. Ableitung<br />
QA1 QA2 QA3<br />
8,0% 11,0% 9,3% 9,3% 8,4% 9,0% 9,0% 8,4%<br />
14,0% 16,8% 17,1% 17,1% 16,8% 17,6% 17,6% 17,8%<br />
20,0% 20,8% 23,3% 23,3% 23,6% 24,2% 24,2% 24,5%<br />
28,0% 21,3% 23,4% 23,4% 24,2% 24,5% 24,5% 25,0%<br />
18,0% 16,0% 15,5% 15,5% 16,0% 15,5% 15,5% 15,6%<br />
9,0% 9,4% 8,0% 8,0% 8,1% 6,7% 6,7% 6,4%<br />
3,0% 4,7% 3,6% 3,6% 3,0% 2,7% 2,7% 2,3%