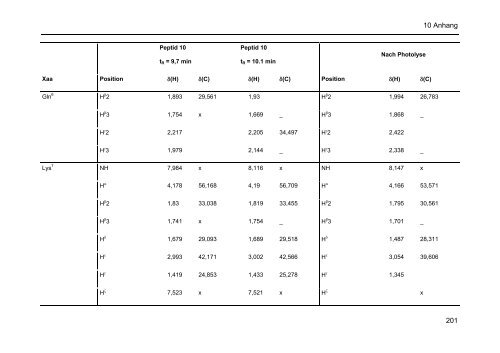
10 Anhang Peptid 10 tR = 9,7 min Peptid 10 tR = 10.1 min Nach Photolyse Xaa Position δ(H) δ(C) δ(H) δ(C) Position δ(H) δ(C) Pro 3 Gly 4 Phe 5 Gln 6 200 H γ NH H α 2 H α 3 NH H α H β H δ H ε H ζ NH H α 1,893 27,41 1,994 27,957 H γ 2,035 24,609 8,464 x 8,449 x NH 8,429 x 4,026 3,932 H α 2 3,916 42,297 3,722 3,733 H α 3 3,853 _ 8,056 x 8,052 NH 8,01 x 4,434 58,623 4,443 58,89 H α 3,109 38,639 3,114 H β 7,162 131,918 H δ 7,072 129,844 H ε 7,328 131,349 H ζ 4,558 55,159 3,085 36,825 7,215 129,064 7,31 128,613 7,266 127,045 8,11 x 8,035 x NH 8,205 x 4,079 56,019 4,167 56,339 H α 4,26 52,838
Peptid 10 tR = 9,7 min Peptid 10 tR = 10.1 min Nach Photolyse Xaa Position δ(H) δ(C) δ(H) δ(C) Position δ(H) δ(C) Gln 6 Lys 7 H β 2 H β 3 H γ 2 H γ 3 NH H α H β 2 H β 3 H δ H ε H γ H ζ 1,893 29,561 1,93 H β 2 1,994 26,783 1,754 x 1,669 _ H β 3 1,868 _ 2,217 2,205 34,497 H γ 2 2,422 1,979 2,144 _ H γ 3 2,338 _ 7,984 x 8,116 x NH 8,147 x 4,178 56,168 4,19 56,709 H α 4,166 53,571 1,83 33,038 1,819 33,455 H β 2 1,795 30,561 1,741 x 1,754 _ H β 3 1,701 _ 1,679 29,093 1,689 29,518 H δ 2,993 42,171 3,002 42,566 H ε 1,419 24,853 1,433 25,278 H γ 7,523 x 7,521 x H ζ 1,487 28,311 3,054 39,606 1,345 x 10 Anhang 201
- Seite 1 und 2:
Neue Methoden zur Sequenzierung fes
- Seite 3:
meinem Großvater Albert Anton Höf
- Seite 6 und 7:
Vorwort Natürlich gibt es ein Lebe
- Seite 8 und 9:
Inhaltsverzeichnis 4 ANALYTIK 47 4.
- Seite 10 und 11:
Inhaltsverzeichnis 8.6 SPR-Experime
- Seite 12 und 13:
Abkürzungen DMF N,N’-Dimethylfor
- Seite 14 und 15:
Abkürzungen TG Tenta Gel Thi Thien
- Seite 16 und 17:
1 Einleitung Echinocandin 2 (Abb. 1
- Seite 18 und 19:
1 Einleitung 1.2 Cyclopeptidbibliot
- Seite 20 und 21:
1 Einleitung 1.3 Die Problematik de
- Seite 22 und 23:
1 Einleitung Eine weitere Möglichk
- Seite 24 und 25:
1 Einleitung 1.4 Fluoreszenzmarkier
- Seite 27 und 28:
2 Aufgabenstellung 2.1 Analytik von
- Seite 29 und 30:
3 Sollbruchstellen 3 Sollbruchstell
- Seite 31 und 32:
3 Sollbruchstellen Abb. 3.3 Der Fmo
- Seite 33 und 34:
3 Sollbruchstellen Die erhaltenen C
- Seite 35 und 36:
3 Sollbruchstellen Abb. 3.8 Ausschn
- Seite 37 und 38:
3 Sollbruchstellen Bestrahlung für
- Seite 39 und 40:
3 Sollbruchstellen HSQC-, TOCSY- un
- Seite 41 und 42:
3 Sollbruchstellen Neben der Bromcy
- Seite 43 und 44:
3 Sollbruchstellen Die Synthese des
- Seite 45 und 46:
3.2.1.1 Der Arylhydrazin-Linker 3 S
- Seite 47 und 48:
3 Sollbruchstellen Aminosäureester
- Seite 49 und 50:
3 Sollbruchstellen Beide Linker wur
- Seite 51 und 52:
3 Sollbruchstellen Zur Erstellung d
- Seite 53 und 54:
3 Sollbruchstellen 39
- Seite 55 und 56:
3 Sollbruchstellen Die Literaturaus
- Seite 57 und 58:
3 Sollbruchstellen Zur anschließen
- Seite 59 und 60:
3 Sollbruchstellen erfolgte die Cyc
- Seite 61 und 62:
4 Analytik 4 Analytik Wie bereits i
- Seite 63 und 64:
4 Analytik Fragmentionen der Seiten
- Seite 65 und 66:
4 Analytik Abb. 4.4 MS(2) Spektrum
- Seite 67 und 68:
4 Analytik Tabelle 4 Peakliste der
- Seite 69 und 70:
4 Analytik Abb. 4.6 Summe aller MS(
- Seite 71 und 72:
N C S Phenylisothiocyanat Kupplung
- Seite 73 und 74:
4 Analytik machen [91-94] . Mit dem
- Seite 75 und 76:
4.2.3.1 Anwendung des Konzepts auf
- Seite 77 und 78:
4 Analytik Abb. 4.11 MALDI-TOF Mass
- Seite 79 und 80:
4 Analytik präparativer RP-HPLC au
- Seite 81 und 82:
4.2.3.3 Anwendung des Konzepts auf
- Seite 83 und 84:
4 Analytik Der Vergleich verschiede
- Seite 85 und 86:
5 Anwendung der Methode 5 Anwendung
- Seite 87 und 88:
5 Anwendung der Methode Bindungstas
- Seite 89 und 90:
5.2 Aufbau einer OBOC-Cyclopeptidbi
- Seite 91 und 92:
5.3 Das Screening 5 Anwendung der M
- Seite 93 und 94:
5 Anwendung der Methode Tabelle 6
- Seite 95 und 96:
5 Anwendung der Methode (pH 7-9.2)
- Seite 97 und 98:
5.4 Die Hitbead-Peptidsequenzen 5 A
- Seite 99 und 100:
Xaa2 Position Xaa3 Xaa4 Xaa5 Xaa6 A
- Seite 101 und 102:
5.5.1 Synthese der ausgesuchten Pep
- Seite 103 und 104:
5 Anwendung der Methode Oberfläche
- Seite 105 und 106:
5 Anwendung der Methode Die Immobil
- Seite 107:
Verbindungsnr. Linear/Cyclisch 5 An
- Seite 110 und 111:
6 Synthese fluoreszenzmarkierter Ph
- Seite 112 und 113:
6 Synthese fluoreszenzmarkierter Ph
- Seite 114 und 115:
6 Synthese fluoreszenzmarkierter Ph
- Seite 116 und 117:
6 Synthese fluoreszenzmarkierter Ph
- Seite 118 und 119:
6 Synthese fluoreszenzmarkierter Ph
- Seite 120 und 121:
6 Synthese fluoreszenzmarkierter Ph
- Seite 122 und 123:
6 Synthese fluoreszenzmarkierter Ph
- Seite 124 und 125:
7 Zusammenfassung und Ausblick sich
- Seite 126 und 127:
7 Zusammenfassung und Ausblick Konz
- Seite 128 und 129:
7 Zusammenfassung und Ausblick Bind
- Seite 130 und 131:
7 Zusammenfassung und Ausblick Auch
- Seite 132 und 133:
8 Experimenteller Teil 1046,54 m/z,
- Seite 134 und 135:
8 Experimenteller Teil 8.2 Allgemei
- Seite 136 und 137:
8 Experimenteller Teil AAV 6 Bestim
- Seite 138 und 139:
8 Experimenteller Teil geladen. Das
- Seite 140 und 141:
8 Experimenteller Teil sowie eine 0
- Seite 142 und 143:
8 Experimenteller Teil AAV 16 Basis
- Seite 144 und 145:
8 Experimenteller Teil für eine St
- Seite 146 und 147:
8 Experimenteller Teil Cyclo[Pll-Gl
- Seite 148 und 149:
8 Experimenteller Teil 8.3.2 Synthe
- Seite 150 und 151:
8 Experimenteller Teil 8.3.3 Synthe
- Seite 152 und 153:
8 Experimenteller Teil 8.3.4 Synthe
- Seite 154 und 155:
8 Experimenteller Teil 8.3.5 Synthe
- Seite 156 und 157:
8 Experimenteller Teil 8.3.7 Synthe
- Seite 158 und 159:
8 Experimenteller Teil 8.3.8.1 Tryp
- Seite 160 und 161:
8 Experimenteller Teil 8.3.8.4 Synt
- Seite 162 und 163:
8 Experimenteller Teil HPQ-Motiv, a
- Seite 164 und 165: 8 Experimenteller Teil 8.3.10 Synth
- Seite 166 und 167: 8 Experimenteller Teil SRBS-pY241 S
- Seite 168 und 169: 8 Experimenteller Teil Fmoc-Pro-Arg
- Seite 170 und 171: 8 Experimenteller Teil 8.4 Modell i
- Seite 172 und 173: 8 Experimenteller Teil 8.5 On-bead-
- Seite 174 und 175: 8 Experimenteller Teil 8.5.3 Enzymg
- Seite 176 und 177: 8 Experimenteller Teil 8.6 SPR-Expe
- Seite 179 und 180: 9 Literaturverzeichnis 9 Literaturv
- Seite 181 und 182: 9 Literaturverzeichnis [64] P. D. W
- Seite 183 und 184: 9 Literaturverzeichnis [133] T. Woh
- Seite 185 und 186: 10 Anhang 10.1 HPLC-offline-MS-Char
- Seite 187 und 188: 10.1.3 Peptid 71 (enzymatische Ring
- Seite 189 und 190: 10.1.5 SPR Peptide 92-97 H-Lys-His-
- Seite 191 und 192: H-Lys-Gln-Pro-His-His-Gly-Glu-βAla
- Seite 193 und 194: H-Lys-His-Pro-Gln-His-Gly-Glu-βAla
- Seite 195 und 196: 10.2 Massenspektren der fluoreszenz
- Seite 197 und 198: 10.3 MALDI-TOF-Massenspektren nach
- Seite 199 und 200: Intens. 800 600 400 200 Intens. 200
- Seite 201 und 202: Intens. x104 1.0 0.8 0.6 0.4 0.2 0.
- Seite 203 und 204: Intens. 1000 800 600 400 200 Intens
- Seite 205 und 206: Intens. 1000 800 600 400 200 0 Inte
- Seite 207 und 208: Intens. 6000 4000 2000 0 Intens. 30
- Seite 209 und 210: 10.4 PTH-Val 10.4.1 1 H-NMR-Spektre
- Seite 211 und 212: 10 Anhang 197
- Seite 213: Peptid 10 tR = 9,7 min Peptid 10 tR
- Seite 217 und 218: 10.6 SPR-Experimente Steady state a