mehr... - Lehrstuhl für Medizinische Informatik - Friedrich-Alexander ...
mehr... - Lehrstuhl für Medizinische Informatik - Friedrich-Alexander ...
mehr... - Lehrstuhl für Medizinische Informatik - Friedrich-Alexander ...
Erfolgreiche ePaper selbst erstellen
Machen Sie aus Ihren PDF Publikationen ein blätterbares Flipbook mit unserer einzigartigen Google optimierten e-Paper Software.
Abschlussarbeitsthema <strong>für</strong> <strong>Informatik</strong>er (M.Sc.):<br />
Entwicklung und Evaluation von Algorithmen zur Identifikation<br />
impliziter Zusammenhänge zwischen GUI-<br />
Elementen in klinischen Formulardaten<br />
Hintergrund<br />
Klinische Routinedaten, also ursprünglich <strong>für</strong> Zwecke der Krankenversorgung erhobene und<br />
dokumentierte Daten, können grundsätzlich auch zur Unterstützung wissenschaftlicher Forschungsvorhaben<br />
in Betracht kommen – im Zusammenhang medizinischer Studien beispielsweise<br />
zu deren Planung oder zur Patientenrekrutierung. Die Auswertung elektronisch<br />
vorliegender Routinedokumentation <strong>für</strong> diese sekundären wissenschaftlichen Zwecke erscheint<br />
besonders vielversprechend, zumal die dann prinzipiell anwendbare automatisierte<br />
Datenverarbeitung ein besonders effizientes und einheitliches Vorgehen ermöglichen kann.<br />
Problem<br />
Während klinische Informationssysteme heutzutage bereits umfangreiche Patientendaten in<br />
strukturierter Form speichern, wird deren automatisierte Integration und Interpretation<br />
praktisch dadurch erschwert, dass die jeweiligen Patientenfakten in den speichernden Datenbanken<br />
überwiegend nicht explizit semantisch ausgezeichnet werden; der Sinn diverser<br />
gespeicherter medizinischer Attribute kann häufig nicht einfach nur aufgrund der technischen<br />
Definition in der zugrundeliegenden Datenbank rekonstruiert werden, sondern ergibt<br />
sich praktisch erst aus dem Kontext der jeweiligen graphischen Formulardarstellung in der<br />
Benutzeroberfläche.<br />
Während eine nachträgliche manuelle Durchsicht und Auszeichnung einzelner Elemente klinischer<br />
Formulare grundsätzlich möglich ist, so wird deren breite systematische Anwendung<br />
ohne geeignete Automatisierungsstrategien durch den resultierenden Arbeitsaufwand erschwert<br />
oder sogar verhindert; alleine am Universitätsklinikum Erlangen (UKER) werden<br />
zahlreiche Formulare mit insg. <strong>mehr</strong> als 70.000 einzelnen Datenelementen eingesetzt – und<br />
werden laufend überarbeitet bzw. ergänzt. Allerdings gestattet bereits die räumliche Anordnung<br />
einzelner GUI-Elementen zueinander gewisse Rückschlüsse hinsichtlich der Interpretation<br />
der jeweils repräsentierten Attribute. Insbesondere stehen beschriftende Elemente regelmäßig<br />
in einem räumlichen Zusammenhang mit den eigentlichen Eingabeelementen<br />
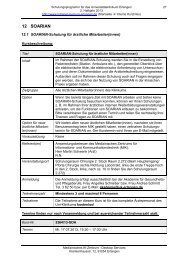
(bspw. darüber oder daneben; siehe Abb. 1 umseitig).<br />
Am UKER sind auch Informationssysteme im Einsatz, deren Formulardefinitionen als XML-<br />
Dokumente repräsentierbar sind, aus denen wiederum die räumliche Anordnung der Bedienelemente<br />
abgeleitet werden kann.<br />
Ziele<br />
In dieser Abschlussarbeit sollen Methoden entwickelt und bewertet werden, die eine automatisierte<br />
Rekonstruktion derartiger impliziter Zusammenhänge aufgrund der räumlichen<br />
Anordnung einzelner Bedienelemente gestatten, die also insbesondere Zusammenhänge<br />
zwischen beschriftenden Elementen und Eingabeelementen explizit machen (artikulieren).
Abb. 1: Bei der Integration und Auswertung elektronisch dokumentierter Patientenfakten<br />
kommt ein beträchtlicher Umfang klinischer Formulare (links) zwar grundsätzlich als Informationsquelle<br />
in Betracht, ist allerdings selbst nicht einfach automatisiert interpretierbar: In<br />
dieser Abschlussarbeit sollen Verfahren entwickelt und bewertet werden, die aufgrund der<br />
räumlichen Anordnung der Bedienelemente implizite Beziehungen rekonstruieren; im abgebildeten<br />
Beispiel gehört etwa das Beschriftungselement „Ruhepuls“ zu einem rechts davon<br />
sichtbaren Eingabeelement mit der Eintragung „180“ (Mitte). Der rechts gezeigte Graph illustriert<br />
ein mögliches Beispiel einer in diesem Fall automatisiert zu erzeugenden Programmausgabe.<br />
Aufgaben<br />
1. Literaturrecherche<br />
2. Einarbeitung in eine beispielhafte Repräsentationsform medizinischer Formulare (XML-<br />
Dokumente aus einem am UKER eingesetzten klinischen Dokumentationssystem)<br />
3. Entwurf und Umsetzung eines technischen Weges zur Definition, Speicherung und Visualisierung<br />
von Zusammenhängen zwischen einzelnen Formularelementen<br />
4. Manuelle Analyse und Definition der Beziehungen zwischen Bedienelementen in einer<br />
Stichprobe (Formulare aus einem am UKER eingesetzten Informationssystem)<br />
5. Entwurf und Umsetzung eines oder <strong>mehr</strong>erer technischer Verfahren(s) zur automatisierten<br />
Erkennung der Beziehungen zwischen Formularelementen aufgrund der räumlichen<br />
Anordnung der Bedienelemente<br />
6. Bewertung des/der entwickelten Verfahren(s) durch Sichtung visualisierter Programmausgaben,<br />
sowie durch Vergleiche der Programmausgaben mit den manuell definierten<br />
Relationen<br />
7. Analyse und Dokumentation der Generalisierbarkeit des/der Verfahren(s)<br />
Anforderungen/Voraussetzungen:<br />
Programmiererfahrung; praktische Erfahrung mit der Verarbeitung von XML-Dokumenten;<br />
Grundkenntnisse der medizinischen <strong>Informatik</strong> – oder die Bereitschaft zur entsprechenden<br />
Einarbeitung.<br />
Kontakt<br />
<strong>Lehrstuhl</strong> <strong>für</strong> <strong>Medizinische</strong> <strong>Informatik</strong>, <strong>Friedrich</strong>-<strong>Alexander</strong>-Universität Erlangen-Nürnberg<br />
Krankenhausstraße 12, 91054 Erlangen<br />
Dr. Dennis Toddenroth:<br />
Dipl.-Inf. Sebastian Mate:<br />
Dennis.Toddenroth@imi.med.uni-erlangen.de<br />
Sebastian.Mate@imi.med.uni-erlangen.de