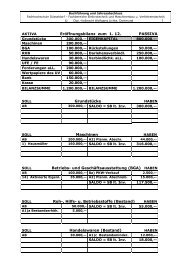
Filterung von Bildern (2D-Filter)
Filterung von Bildern (2D-Filter)
Filterung von Bildern (2D-Filter)
Erfolgreiche ePaper selbst erstellen
Machen Sie aus Ihren PDF Publikationen ein blätterbares Flipbook mit unserer einzigartigen Google optimierten e-Paper Software.
Bildverarbeitung und Biometrik <br />
Prof. Dr.-Ing. Thomas Zielke "<br />
<strong><strong>Filter</strong>ung</strong> <strong>von</strong> <strong>Bildern</strong><br />
(<strong>2D</strong>-<strong>Filter</strong>)<br />
Bildverarbeitung und Biometrik<br />
SS13 5.1
Optische <strong>Filter</strong> <br />
(Quelle: Produktinformation Rodenstock-<strong>Filter</strong>)"<br />
Beispiel Skylightfilter<br />
Weil das Himmelslicht im Schatten einen zu<br />
hohen Anteil an kurzen und einen zu<br />
geringen Anteil an langen Wellenlängen hat,<br />
ist für farbneutrale Farbdias ein <strong>Filter</strong> nötig,<br />
dessen Lichtdurchlässigkeit wie im<br />
Diagramm unten zu kurzen Wellenlängen<br />
hin kontinuierlich abnimmt. Der Blaustich<br />
verschwindet, die Fotos werden so<br />
farbneutral wie bei Digitalkameras mit<br />
automatischem Weißabgleich.<br />
Bildverarbeitung und Biometrik<br />
SS13 5.2
<strong><strong>Filter</strong>ung</strong> eines Bildes <br />
Implementierungsalternativen (lineare <strong>Filter</strong>)"<br />
Bei der <strong><strong>Filter</strong>ung</strong> eines Bildes werden die Bildpunkte (Pixel)<br />
in Abhängigkeit <strong>von</strong> ihrer Nachbarschaft manipuliert.<br />
Ortsraum<br />
• Direkte Manipulation der Pixelwerte im Bildbereich<br />
Frequenzraum<br />
• Bildtransformation (z.B. Diskrete Fourier Transformation / DFT)<br />
• Manipulation der Transformierten<br />
• Rücktransformation in den Bildbereich<br />
Eine <strong>Filter</strong>operation ist im Frequenzraum bedeutend weniger rechenaufwendig als im<br />
Ortsraum. Jedoch ist bei <strong>Filter</strong>operationen, die nur eine kleine Bildnachbarschaft<br />
einbeziehen, der fixe Aufwand für die Bildtransformationen i.d.R. größer als der<br />
Aufwand für die Berechnung der <strong><strong>Filter</strong>ung</strong> selbst.<br />
Bildverarbeitung und Biometrik<br />
SS13 5.3
Erzeugung einer Frequenzraumdarstellung (1) <br />
Diskrete <strong>2D</strong> Fourier-Transformation"<br />
Die zweidimensionale diskrete Fourier-Transformation<br />
eines (Grauwert-)Bildes G(r,c) ist definiert als:<br />
F(u, v) = 1<br />
r und c sind die<br />
Indizes der<br />
Bildzeilen bzw.<br />
Bildspalten.<br />
N<br />
N !1 N!1<br />
# #<br />
r=0 c= 0<br />
G(r, c) e<br />
u und v sind<br />
Ortsfrequenzen<br />
entlang der<br />
Bildspalten bzw.<br />
Bildzeilen.<br />
!i 2" (ur+ v c )<br />
N<br />
e<br />
ist die Basis des<br />
natürlichen<br />
Logarithmus<br />
(ca. 2,71828) und<br />
i = !1 ist die<br />
imaginäre<br />
Koordinate für eine<br />
komplexe Zahl.<br />
Bildverarbeitung und Biometrik<br />
SS13 5.4
Erzeugung einer Frequenzraumdarstellung (2) <br />
Diskrete <strong>2D</strong> Fourier-Transformation"<br />
F(u, v) = 1<br />
N<br />
N !1<br />
#<br />
r=0<br />
N!1<br />
#<br />
c= 0<br />
(ur+ v c )<br />
!i 2"<br />
N<br />
G(r, c) e<br />
Die Fourier-Transformation ist invertierbar (umkehrbar).<br />
Das Originalbild kann durch Rücktransformation in den<br />
Ortsraum wieder hergestellt werden.<br />
Die komplexe Fourier-Transformierte F(u,v)<br />
kann auch als Summe des Realteils R(u,v) und<br />
des Imaginärteils I(u,v) ausgedrückt werden:<br />
F(u, v) = R(u, v) + i I(u, v)<br />
Bildverarbeitung und Biometrik<br />
SS13 5.5
Allgemeine Form einer komplexen Zahl:<br />
1. Komponentendarstellung<br />
(Realteil und Imaginärteil)<br />
2. Darstellung durch Betrag und Winkel<br />
in der komplexen Ebene<br />
Betrag:<br />
Exkurs: Komplexe Zahlen"<br />
Euler-Identität:<br />
Phase:<br />
Bildverarbeitung und Biometrik<br />
SS13 5.6
Erzeugung einer Frequenzraumdarstellung (3) <br />
Fourierspektrum (Spektrum der Ortsfrequenzen)"<br />
Den Betrag der komplexen Fourier-Transformierten bezeichnet man<br />
als Fourierspektrum (auch "Amplitudenspektrum" oder "Spektrum"):<br />
P(u, v) = [R(u, v)] 2 +[I(u, v)] 2<br />
Leistungsspektrum (power spectrum):<br />
512 × 512<br />
| F(u, v) | = [R(u, v)] 2 +[I(u, v)] 2<br />
u<br />
Bildverarbeitung und Biometrik<br />
SS13 5.7<br />
v
Verschiedene Sinusgitter <br />
und ihre Frequenzbilddarstellung"<br />
Der Betrag der Fourier-Transformierten<br />
kann als ein "Frequenz-Bild" dargestellt<br />
werden.<br />
Das Frequenzbild ist radialsymmetrisch<br />
bzgl. seines Ursprungs, des Null-<br />
Frequenz-Punkts ("DC"-Komponente).<br />
Horizontale (vertikale) Frequenzen im<br />
Ortsraum werden im Frequenzbild<br />
entlang der horizontalen (vertikalen)<br />
Achse aufgetragen.<br />
Bildverarbeitung und Biometrik<br />
SS13 5.8
Originalbild<br />
Frequenzbilddarstellung eines Bildes aus <br />
unterschiedlichen lokalen Sinusmustern "<br />
Fourier-<br />
Transformation<br />
und<br />
anschließende<br />
Betragsbildung<br />
Betrag der<br />
Fourier-Transformierten<br />
Bildverarbeitung und Biometrik<br />
SS13 5.9
<strong><strong>Filter</strong>ung</strong> mit Hilfe der Fourier-Transformation (1) <br />
(Quelle: The Scientist and Engineer's Guide to Digital Signal Processing)"<br />
Bildverarbeitung und Biometrik<br />
SS13 5.10
<strong><strong>Filter</strong>ung</strong> mit Hilfe der Fourier-Transformation (2) <br />
(Quelle: The Scientist and Engineer's Guide to Digital Signal Processing)"<br />
Bildverarbeitung und Biometrik<br />
SS13 5.11
Prinzip der diskreten zweidimensionalen Faltung <br />
(Örtliche Faltung / Spatial Convolution)"<br />
<strong>Filter</strong>maske<br />
(3 × 3)<br />
w -1,-1 w -1,0 w -1,1<br />
w 0,-1 w 0,0 w 0,1<br />
Eingangsbild<br />
Bei der Faltung berechnet sich jeder Pixel<br />
des Ausgangsbildes als gewichtete<br />
Summe der Pixel einer Bildnachbarschaft.<br />
Die Gewichte sind die Koeffizienten der<br />
<strong>Filter</strong>maske (des <strong>Filter</strong>kerns).<br />
w 1,-1 w 1,0 w 1,1 <strong>Filter</strong>koeffizienten (Gewichte)<br />
×<br />
Ausgangsbild<br />
Bildverarbeitung und Biometrik<br />
SS13 5.12
Eingangsbild Ii,j<br />
I 0,0 I 0,1 I 0,2 … I 0,M<br />
I 1,0 I 1,1 …<br />
I 2,0<br />
:<br />
…<br />
I N,0 … I N,M<br />
Berechnung der diskreten Faltung "<br />
W / 2<br />
"<br />
p= !W / 2<br />
<strong>Filter</strong>maske Mp,q<br />
M -1,-1 M -1,0 M -1,1<br />
M 0,-1 M 0,0 M 0,1<br />
M 1,-1 M 1,0 M 1,1<br />
Maskengröße W = 3<br />
W / 2<br />
"<br />
q= !W / 2<br />
Ausgangsbild Oi,j<br />
O 0,0 O 0,1 O 0,2 … O 0,M<br />
O 1,0 O 1,1 …<br />
O 2,0<br />
:<br />
…<br />
O N,0 … O N,M<br />
O[i, j] = I[i<br />
+ p, j + q]# M[p, q]<br />
Bildverarbeitung und Biometrik<br />
SS13 5.13
Prinzip des Faltungsprozesses "<br />
Masken-<br />
zentrum<br />
×<br />
×<br />
Die Faltung des Bildes mit dem<br />
<strong>Filter</strong>kern an einer Bildposition<br />
liefert den Bildwert an der jeweils<br />
gleichen Position im Ergebnisbild.<br />
Für die <strong><strong>Filter</strong>ung</strong> des kompletten<br />
Bildes wird die Maske sukzessiv<br />
über alle Bildpositionen platziert.<br />
×<br />
Bildverarbeitung und Biometrik<br />
SS13 5.14
Konvolution mit <strong>Filter</strong>masken <br />
Randbetrachtungen "<br />
Je nach Größe der <strong>Filter</strong>maske<br />
existiert ein Bildrand (min. 1 Pixel<br />
breit), dessen Pixel nicht normal<br />
berechnet werden können, weil<br />
ein Teil der Maske außerhalb des<br />
Eingangsbildes liegt.<br />
Gängige Methoden der<br />
Randbehandlung:<br />
keine Randbetrachtung<br />
Zero-Padding<br />
Last-Value<br />
Periodische Fortsetzung<br />
Symmetrische Fortsetzung<br />
Interpolative Fortsetzung<br />
Konstruktion spezieller <strong>Filter</strong>masken<br />
?<br />
?<br />
Bildverarbeitung und Biometrik<br />
SS13 5.15
Tiefpass<br />
• Unterdrückung <strong>von</strong><br />
hohen Frequenzen<br />
(feinen Details)<br />
Ideale und nichtideale<br />
1D-<br />
<strong>Filter</strong>funktion im<br />
Frequenzbereich<br />
Hochpass<br />
• Unterdrückung<br />
<strong>von</strong> niedrigen<br />
Frequenzen<br />
(<strong>von</strong> groben<br />
Strukturen und<br />
dem Gleichanteil)<br />
Lineare <strong>Filter</strong> (1)"<br />
Bildverarbeitung und Biometrik<br />
SS13 5.16
Bandpass<br />
• Unterdrückung<br />
<strong>von</strong> hohen und<br />
niedrigen<br />
Frequenzen<br />
Bandstop<br />
• Unterdrückung<br />
<strong>von</strong><br />
Mittenfrequenzen<br />
Lineare <strong>Filter</strong> (2)"<br />
Ideales eindimensionales<br />
Bandpass-<strong>Filter</strong> im Frequenzbereich<br />
Ideales 1D-<br />
Bandstop-<strong>Filter</strong> im<br />
Frequenzbereich<br />
Bildverarbeitung und Biometrik<br />
SS13 5.17
Anwendung eines Bandstop-<strong>Filter</strong>s <br />
Beispiel: Bildrestauration"<br />
Unterdrückung<br />
der<br />
Störfrequenz<br />
Verarbeitungsschritte mit ImageJ:<br />
• Bild um 34º im Uhrzeigersinn rotieren, damit die Streifen horizontal ausgerichtet<br />
werden.<br />
• Plugin "FFT-<strong>Filter</strong>" aufrufen.<br />
• "Suppress stripes in one direction" auf "horizontal" einstellen (die Streifenfrequenz<br />
wird vom Programm automatisch bestimmt).<br />
• <strong>Filter</strong> für kleine Strukturen auf Minimal stellen, <strong>Filter</strong> für große Strukturen auf<br />
halbe Bildbreite ("FFT-<strong>Filter</strong>" ist eigentlich ein Bandpassfilter, das hier nicht<br />
benutzt werden soll).<br />
Bildverarbeitung und Biometrik<br />
SS13 5.18
Diskrete Tiefpass-<strong>Filter</strong> <br />
(<strong>Filter</strong>masken)"<br />
Glättungseffekt (Smoothing, Blur)<br />
Koeffizienten sind ausnahmslos positiv<br />
Koeffizienten sind normalisiert<br />
(Summe aller Koeffizienten ergibt 1)<br />
Beispiel: Mittelwertfilter<br />
3 × 3<br />
5 × 5<br />
Bildverarbeitung und Biometrik<br />
SS13 5.19
Mittelwertfilter <br />
(Beispiel)"<br />
Original <strong><strong>Filter</strong>ung</strong>sergebnis<br />
mit 3×3 Maske<br />
<strong><strong>Filter</strong>ung</strong>sergebnis<br />
mit 5×5 Maske<br />
Bildverarbeitung und Biometrik<br />
SS13 5.20
Gaußsches Glättungsfilter <br />
(Gaussian smoothing filter)"<br />
Zweidimensionale diskrete Gaußfunktion mit Mittelwert 0:<br />
g[l, k] = !( l 2 + k 2 )/ (2" 2 e<br />
)<br />
<strong>Filter</strong>maske:<br />
M[p, q] =<br />
! !<br />
p q<br />
g[p, q]<br />
g[ p, q]<br />
σ (sigma) =<br />
"<strong>Filter</strong>breite"<br />
Bildverarbeitung und Biometrik<br />
SS13 5.21
Gaußsches Glättungsfilter <br />
Beispiel"<br />
Original 5 × 5 , σ = 1 9 × 9 , σ = 2<br />
Bildverarbeitung und Biometrik<br />
SS13 5.22
α<br />
Verstärkungsfaktor<br />
Anwendung des Tiefpassfilters <br />
für das Schärfen (sharpening) eines Bildes"<br />
"Unsharp Masking" - Verfahren<br />
Eingangsbild<br />
Tiefpass<br />
(lowpass)<br />
<strong><strong>Filter</strong>ung</strong><br />
× –<br />
σ<br />
Sigma des<br />
Tiefpassfilters<br />
Ergebnisbild<br />
Bildverarbeitung und Biometrik<br />
SS13 5.23
Unscharfe Maske (Unsharp Masking) <br />
Bildbeispiele"<br />
Bildverarbeitung und Biometrik<br />
SS13 5.24
Diskrete Hochpass-<strong>Filter</strong>"<br />
Betonung <strong>von</strong> Kanten (Grauwertänderungen)<br />
Unterdrückung <strong>von</strong> homogenen Flächen<br />
Die <strong>Filter</strong>maske hat positive und negative<br />
Koeffizienten<br />
Die <strong>Filter</strong>koeffizienten sind normalisiert<br />
Summe der Koeffizienten ergibt 0<br />
Beispiel: Differenzfilter<br />
-1 -1 -1<br />
-1 8 -1<br />
-1 -1 -1<br />
Bildverarbeitung und Biometrik<br />
SS13 5.25
-1 -1 -1<br />
-1 8 -1<br />
-1 -1 -1<br />
Differenzfilter <br />
Beispiel"<br />
<strong>Filter</strong>ergebnis<br />
vorzeichenbehaftet<br />
(Nullwert des gefilterten<br />
Bildes in dieser Darstellung bei<br />
Grauwert 100)<br />
<strong>Filter</strong>ergebnis<br />
Absolutwert<br />
Bildverarbeitung und Biometrik<br />
SS13 5.26
Differenzierung eines kontinuierlichen 1D-Signals"<br />
S(x)<br />
S'(x) =<br />
! S<br />
! x<br />
S''(x) = ! 2 S<br />
! x 2<br />
Zeitlicher oder örtlicher<br />
Signalverlauf<br />
x<br />
1. Ableitung nach x<br />
x<br />
2. Ableitung nach x<br />
x<br />
Bildverarbeitung und Biometrik<br />
SS13 5.27
Ableitungsfilter (1)"<br />
Gradient<br />
in einem Punkt (x,y) einer<br />
zweidimensionalen kontinuierlichen<br />
Funktion (Ableitungsvektor)<br />
! f (x, y)= G[ f (x, y)] =<br />
"<br />
$<br />
$<br />
# $<br />
G x<br />
G y<br />
" ( f<br />
% $<br />
( x<br />
' $<br />
' =<br />
$<br />
& ' ( f<br />
$<br />
# $ ( y<br />
%<br />
'<br />
'<br />
'<br />
'<br />
& '<br />
Richtungsableitungen<br />
Bildverarbeitung und Biometrik<br />
SS13 5.28
Ableitungsfilter (2)"<br />
Betrag des Gradienten an einem Punkt (x,y) einer<br />
zweidimensionalen kontinuierlichen Funktion:<br />
!f (x,y) = G[f (x,y)] = G<br />
2<br />
+<br />
2<br />
x<br />
Gy<br />
Richtung des Gradienten an einem Punkt (x,y)<br />
einer zweidimensionalen kontinuierlichen Funktion:<br />
!(x, y) =tan "1 G # & y<br />
% (<br />
$ '<br />
G x<br />
Bildverarbeitung und Biometrik<br />
SS13 5.29
Ergebnis mit<br />
einfachem<br />
Ableitungsfilter<br />
Ergebnis mit "second<br />
derivative operator"<br />
z.B. "Laplace <strong>Filter</strong>"<br />
Helligkeitskeitssteigung<br />
(brightness slope)"<br />
Helligkeitssteigung an<br />
zwei benachbarten Pixeln<br />
Bildverarbeitung und Biometrik<br />
SS13 5.30
Maske für horizontale<br />
2. Ableitung<br />
Diskrete Ableitung in <strong>2D</strong> <br />
(Numerische Approximation)"<br />
Horizontale Maske<br />
Vertikale<br />
Maske<br />
Bildverarbeitung und Biometrik<br />
SS13 5.31
Kombination einer<br />
horizontalen und einer<br />
vertikalen Faltung durch<br />
Addition der <strong>Filter</strong>masken:<br />
( 1 !2 1)<br />
+<br />
Herleitung <strong>von</strong> <strong>Filter</strong>masken <br />
Beispiel: 3×3 Laplace - Operator"<br />
Allgemeiner<br />
Laplace-Operator:<br />
" 1 %<br />
$ '<br />
$<br />
!2<br />
$ '<br />
# 1 &<br />
=<br />
" 0 0 0%<br />
$<br />
$<br />
1<br />
$<br />
# 0<br />
!2<br />
0<br />
'<br />
1<br />
'<br />
0&<br />
+<br />
" 0 1 0%<br />
$<br />
$<br />
0<br />
$<br />
# 0<br />
!2<br />
1<br />
'<br />
0<br />
'<br />
0&<br />
=<br />
" 0 1 0%<br />
$<br />
$<br />
1<br />
$<br />
# 0<br />
!4<br />
1<br />
'<br />
1<br />
'<br />
0&<br />
Subtraktion des Laplacegefilterten<br />
Bildes vom Original:<br />
! 0 0 0$<br />
#<br />
#<br />
0<br />
#<br />
" 0<br />
1<br />
0<br />
0<br />
&<br />
&<br />
0%<br />
'<br />
! 0 1 0$<br />
#<br />
#<br />
1<br />
#<br />
" 0<br />
'4<br />
1<br />
1<br />
&<br />
&<br />
0%<br />
=<br />
! 0 '1 0 $<br />
#<br />
#<br />
'1<br />
#<br />
" 0<br />
5<br />
'1<br />
'1<br />
&<br />
&<br />
0 %<br />
Bildverarbeitung und Biometrik<br />
SS13 5.32
0 0 -1 0 0<br />
0 -1 -2 -1<br />
-1 -2 16 -2<br />
0 -1 -2 -1<br />
0 0 -1 0<br />
0<br />
-1<br />
0<br />
0<br />
Laplace - <strong>Filter</strong> <br />
(Mexican Hat)"<br />
Das Laplace-<strong>Filter</strong> ist ein isotropes<br />
2-fach differenzierendes <strong>Filter</strong>!<br />
-1 -1 -1<br />
-1 8 -1<br />
-1 -1 -1<br />
0 -1 0<br />
-1 4 -1<br />
0 -1 0<br />
Bildverarbeitung und Biometrik<br />
SS13 5.33
Einfache Ableitungsfilter <br />
Roberts Operatoren"<br />
Bildverarbeitung und Biometrik<br />
SS13 5.34
Anwendung des Roberts Operators <br />
auf Binärbilder"<br />
G[ B[i, j] ]= (B[i, j]! B[i +1, j +1]) 2 + (B[i +1, j] ! B[i, j +1]) 2<br />
G[ B[i, j] ]= B[i, j] ! B[i +1, j +1] + B[i +1, j]! B[i, j +1]<br />
Bildverarbeitung und Biometrik<br />
SS13 5.35
Sobel - Operator"<br />
-1 -2 -1<br />
0 0 0<br />
1 2 1<br />
Zeilenmaske<br />
-1 0 1<br />
-2 0 2<br />
-1 0 1<br />
Spaltenmaske<br />
Bildverarbeitung und Biometrik<br />
SS13 5.36
Kantenextraktion <br />
Binarisierung des Ableitungsbildes"<br />
Ergebnis der Sobel-<strong><strong>Filter</strong>ung</strong> Schwellwert τ = 40<br />
Bildverarbeitung und Biometrik<br />
SS13 5.37
Binarisierung des Ableitungsbildes <br />
zur Kantenextraktion <br />
Wahl des Schwellwertes ist entscheidend!"<br />
Bildverarbeitung und Biometrik<br />
SS13 5.38
Multiskalen-Bildanalyse / Auflösungspyramide <br />
(multiscale image analysis / resolution pyramid)"<br />
Bedeutsame<br />
Bildinformation existiert<br />
auf mehreren<br />
Auflösungsebenen<br />
(Skalen).<br />
In einem Porträtbild<br />
z.B. sind bei hoher<br />
Auflösung die Augen<br />
zu erkennen, bei sehr<br />
niedriger Auflösung nur<br />
die Form des Kopfes<br />
und des Oberkörpers.<br />
Bildverarbeitung und Biometrik<br />
SS13 5.39
Multiskalen-Kantenfilterung <br />
ImageJ "Find Edges": Berechnung des Gradientenbetrags mit Hilfe <strong>von</strong> 3x3 Sobel-Masken"<br />
Viele Kanten (= starke Gradienten)<br />
existieren auf mehreren Skalen<br />
(Auflösungsebenen).<br />
Andere Kanten existieren nur auf<br />
bestimmten bzw. wenigen Skalen.<br />
2736 x 1824 Pixel 684 x 456 Pixel 171 x 114 Pixel<br />
Bildverarbeitung und Biometrik<br />
SS13 5.40
Difference of two successive<br />
images in the Gaussian<br />
pyramid<br />
The Laplacian Pyramid as a Compact Image Code <br />
PETER J. BURT, EDWARD H. ADELSON, <br />
IEEE TRANSACTIONS ON COMMUNICATIONS, VOL. COM-3l, NO. 4, APRIL 1983 <br />
"<br />
Gaussian Pyramid Laplacian Pyramid<br />
Gaussian Pyramid<br />
Laplacian Pyramid<br />
Bildverarbeitung und Biometrik<br />
SS13 5.41
Multiskalen-Bildrepräsentationen"<br />
Die Fourier-Transformation zerlegt ein Signal in seine<br />
Frequenzkomponenten. Damit werden die Energieanteile des<br />
Signals auf beliebigen "Skalen" explizit dargestellt.<br />
Ein großer Nachteil dieser Repräsentation ist der völlige Verlust des<br />
Zugangs zur Ortsinformation. Die Frequenzkomponenten sind im<br />
Bild nicht lokalisiert.<br />
Die Laplace-Pyramide ist eine Multiskalen-Repräsentation, deren<br />
Komponenten sowohl bezüglich des Orts als auch der Ortsfrequenz<br />
lokalisiert sind.<br />
Aus der Laplace-Pyramide kann, wie aus der Fourier-<br />
Transformierten, das Originalbild rekonstruiert werden. Diese<br />
Eigenschaft garantiert die Vollständigkeit einer Repräsentation.<br />
Die Vorteile der Fourier-Transformation und der Laplace-Pyramide<br />
werden <strong>von</strong> der "Wavelet-Transformation" vereint. Die Wavelet-<br />
Theorie begründet weitere Vorteile dieser Repräsentation.<br />
Bildverarbeitung und Biometrik<br />
SS13 5.42
Wavelet- und Fourier-Transformation im Vergleich <br />
(Andreas Niemöller, Die Wavelet-Analyse als chemometrisches Werkzeug:<br />
Analytische Anwendungen in der NIR-Spektrometrie,<br />
http://duepublico.uni-duisburg-essen.de/servlets/DerivateServlet/Derivate-5254/inhalt.htm) <br />
Schematische Darstellung der<br />
Ausdehnung <strong>von</strong> Zeit-Frequenz-<br />
Fenstern (1D/Zeitsignal):<br />
a) im Zeitbereich,<br />
b) nach Fourier-Transformation,<br />
c) nach gefensterter Fourier-<br />
Transformation und<br />
d) nach Wavelet-Transformation.<br />
Bildverarbeitung und Biometrik<br />
SS13 5.43
Was sind Wavelets ("kleine Wellen") ?"<br />
Wavelets werden zur Repräsentation <strong>von</strong> Funktionen benutzt #<br />
Zerlegung der Funktionen in bestimmte Funktionsanteile ähnlich wie bei der<br />
Fourieranalyse.<br />
Die Funktionsanteile sind bei der Fourieranalyse die Sinus- und<br />
Kosinusfunktionen, bei der Wavelet-Transformation sind es<br />
Funktionsanteile, die sowohl im Ortsbereich, als auch im<br />
Frequenzbereich räumlich begrenzte Intervalle der Funktionen<br />
darstellen.<br />
Wavelets werden in Familien eingeteilt, die jeweils auf einem Mutter-<br />
Wavelet aufbauen. Aus diesem Mutter-Wavelet entsteht die Familie,<br />
indem Ausdehnung, Verschiebung und Orientierung (<strong>2D</strong>) des Mutter-<br />
Wavelets variiert werden.<br />
Bildverarbeitung und Biometrik<br />
SS13 5.44
Was sind Wavelets ("kleine Wellen") ?"<br />
Ein eindimensionales Mutter-Wavelet ψ :<br />
Eine Wavelet-Familie wird durch das<br />
Mutter-Wavelet und eine Menge <strong>von</strong><br />
gestauchten und verschobenen<br />
Kopien des Mutter-Wavelets gebildet:<br />
Bildverarbeitung und Biometrik<br />
SS13 5.45





![Dokument [PDF, 14,8 MB] - Fachbereich Maschinenbau und ...](https://img.yumpu.com/22476839/1/184x260/dokument-pdf-148-mb-fachbereich-maschinenbau-und-.jpg?quality=85)


![Skript [605 kB] - FB 4 Allgemein](https://img.yumpu.com/21942099/1/184x260/skript-605-kb-fb-4-allgemein.jpg?quality=85)


![2 Wärmeschutz [559 kB] - Fachhochschule Düsseldorf](https://img.yumpu.com/20681304/1/190x135/2-warmeschutz-559-kb-fachhochschule-dusseldorf.jpg?quality=85)


![Dokument [PDF, 9,1 MB] - FB 4 Allgemein - Fachhochschule ...](https://img.yumpu.com/17999083/1/184x260/dokument-pdf-91-mb-fb-4-allgemein-fachhochschule-.jpg?quality=85)