Identifizierung und Charakterisierung von neuen Genen für die ...
Identifizierung und Charakterisierung von neuen Genen für die ... Identifizierung und Charakterisierung von neuen Genen für die ...
- 88 - Hinzufügen von β-Galactosidase-Enzym (lacZ) im fortlaufenden Leseraster und Neomycin- Resistenz: KpnI (9792) Xho I (9773) SalI (9767) Thymidine-Kinase Eco RI (7718) pBS II-KS + TK + 5’-Flanke Spe I geschnitten und mit Klenow-Enzym geblunted + Xba I geschnitten Ampicillin pBS II-KS + TK + 5'-Flanke + lacZ-Neo.trunc 5'-Flanke Start des Gens TRIM46 auf der genomischen Sequenz der 5’-Flanke: Das β-Galactosidase-Enzym (lacZ) wurde so geschnitten und mit Klenow-Enzym zubereitet, dass es bei der Klonierung in den Zielvektor an die 5’-Flanke im fortlaufenden Leseraster mit der dort beginnenden kodierenden Sequenz von TRIM46 fusionierte. Der korrekte Übergang wurde durch Sequenzierung überprüft. 5’…ATGGCTGAGGGTGAGGATATGCAGACCTTCACTTCCATCATGGATGCACTAGTCCGCATCAGT…3’ Schnittstelle Spe I: 5’…A^CTAG T…3’ => 5’…A blunt: 5’…ACTAG 3’…T GATC^A…5’ …TGATC 3’…TGATC Anfang der lacZ-Sequenz in pKC414-lacZ-Neo: 5’…GGGCCCCCCGGGGGTACCTCTAGAATGCATTCCGCGGGTTTTCATGTACCCAGCATGGGGGATCCCGT CGTTTTA…3’ Schnittstelle Acc 65I: 11994 bp ATG Not I (670) Xba I (677) Acc 65I (26) SmaI (22) ApaI (18) KpnI (12) Acc65I (8) pGK-Neomycin-truncated SpeI (1762) Acc 65I (9788) Bam HI (2027) SacI (8930) Bam HI (7712) SacI (7416) PvuI (11449) KpnI (6594) Acc 65I (6590) SacI (657) Pvu I (500) KpnI (5532) Acc 65I (5528) ORF PvuI (5370) Bam HI (5481) Xba I (5522) Eco RI (2483) SacI (3555) PvuI (3711) lacZ-pA Pvu I (4164) Pvu I (4644) Sa cII (4 8) BamHI (73) pKC414-lacZ-Neo β-Galactosidase-Enzym (lacZ) und Neomycin-Resistenzgen wurden aus dem Vektor pKC414 durch Acc 65I und Xba I herausgeschnitten, wobei die Acc 65I- Schnittstelle mit Klenow-Enzym geblunted wurde. 5’…G^GTAC C…3’ => GTACC…3’ blunt: GTACC…3’ 3’…C CATG^G…5’ G…5’ CATGG…5’ KpnI (30) XbaI (32) lacZ-pA EcoRI (3071) 5207 bp Sp eI (3792) BamHI (3527) pGK-Neomycin-pA Xba I (4877) XhoI (5163) Sp eI (5169 ) XhoI (5175) EcoRV (1180) NotI (5182)
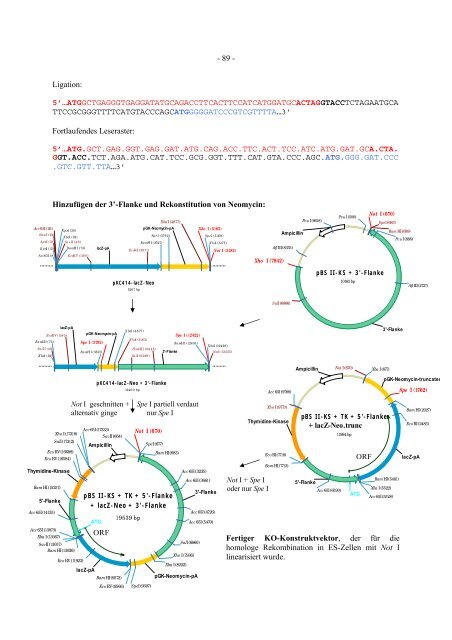
Acc 65I (26) SmaI (22) ApaI (18) KpnI (12) Acc65I (8) BamHI (73) Sa cII (48) XbaI (32) Ligation: - 89 - 5’…ATGGCTGAGGGTGAGGATATGCAGACCTTCACTTCCATCATGGATGCACTAGGTACCTCTAGAATGCA TTCCGCGGGTTTTCATGTACCCAGCATGGGGGATCCCGTCGTTTTA…3’ Fortlaufendes Leseraster: 5’…ATG.GCT.GAG.GGT.GAG.GAT.ATG.CAG.ACC.TTC.ACT.TCC.ATC.ATG.GAT.GCA.CTA. GGT.ACC.TCT.AGA.ATG.CAT.TCC.GCG.GGT.TTT.CAT.GTA.CCC.AGC.ATG.GGG.GAT.CCC .GTC.GTT.TTA…3’ Hinzufügen der 3’-Flanke und Rekonstitution von Neomycin: KpnI (30) XbaI (32) Sa cII (48) lacZ-pA EcoR V (118 0) Thymidine-Kinase Bam HI (15257) 5'-Flanke Acc 65I (14135) Acc 65I (13073) Xba I (13067) BamHI (73) Xho I (17318) SalI (17312) Eco RV (16688) EcoRV (16584) SacII (13057) Bam HI (13026) EcoRV (1180) lacZ-pA pGK-Neomycin-pA EcoRI (3071) pKC414-lacZ-Neo 5207 bp pGK-Neomycin-pA BamH I (3527) pKC414-lacZ-Neo + 3'-Flanke 1246 0 bp XbaI (4877) Sp e I (3792) Sp eI (5169) 3'-Flanke Not I geschnitten + Spe I partiell verdaut alternativ ginge nur Spe I Eco RV (11923) Spe I (3792) BamHI (3527) Acc 65I (17333) SacII (664) XbaI (4877) XhoI (5163) Hind III (804 5) Sa lI (6239 ) pBS II-KS + TK + 5'-Flanke + lacZ-Neo + 3'-Flanke lacZ-pA Ampicillin ATG ORF Bam HI (9572) Eco RV (9566) 19539 bp Not I (670) SpeI (9307) SpeI (677) Bam HI (683) Spe I (12422) BamHI (12416) Xba I (8222) Acc 65I (3235) Xho I (7936) pGK-Neomycin-pA Acc 65I (3661) SalI (6860) Xho I (5163) 3'-Flanke Acc 65I (4726) Acc 65I (5470) XhoI (5175) Not I (5182) XbaI (12428) NotI (12435) Xho I (7942) Not I + Spe I oder nur Spe I Ampicillin Afl III (8355) SalI (6866) Acc 65I (9788) Xho I (9773) Thymidine-Kinase Eco RI (7718) Bam HI (7712) Pvu I (9618) Ampicillin Pvu I (500) pBS II-KS + 3'-Flanke 10163 bp Not I (670) SpeI (683) pBS II-KS + TK + 5'-Flanke + lacZ-Neo.trunc 5'-Flanke Acc 65I (6590) Not I (670) 11994 bp ATG ORF Xba I (677) Xba I (5522) Bam HI (689) 3'-Flanke Acc 65I (5528) Fertiger KO-Konstruktvektor, der für die homologe Rekombination in ES-Zellen mit Not I linearisiert wurde. Pvu I (886) Afl III (2737) pGK-Neomycin-truncated Bam HI (5481) Spe I (1762) Bam HI (2027) Eco RI (2483) lacZ-pA
- Seite 37 und 38: - 37 - Vorhersage neuer Marker-Gene
- Seite 39 und 40: - 39 - 90 IMAGp998I113134 Hippocamp
- Seite 41 und 42: E 14 - 41 - A B C Abbildung 41: In-
- Seite 43 und 44: E18 E14 Klon 149 - unbekanntes Gen
- Seite 45 und 46: - 45 - Die 3376 bp lange cDNA-Seque
- Seite 47 und 48: E 18 - 47 - M CGL M CGL M CGL A B C
- Seite 49 und 50: E18 E16 E14 - 49 - Positivkontrolle
- Seite 51 und 52: - 51 - Die Sequenz des IMAGE-Klons
- Seite 53 und 54: - 53 - Bestimmung von Splicevariant
- Seite 55 und 56: - 55 - ATGGGACTCTCATCTCACCAGCTGCATA
- Seite 57 und 58: - 57 - Übersicht der 8 Splicevaria
- Seite 59 und 60: Abbildung 53: 1 - 100 bp Marker 2 -
- Seite 61 und 62: - 61 - Haupt-Splicevariante 2 (enth
- Seite 63 und 64: - 63 - Auf der Seite davor sind Sta
- Seite 65 und 66: - 65 - In Übereinstimmung mit der
- Seite 67 und 68: - 67 - Die ProDom-Protein-Datenbank
- Seite 69 und 70: - 69 - Bei TRIM46 allerdings schien
- Seite 71 und 72: - 71 - “Neural Cell Adhesion Mole
- Seite 73 und 74: - 73 - Abbildung 57: Übersicht der
- Seite 75 und 76: - 75 - Suche nach Protein-Interakti
- Seite 77 und 78: - 77 - Die Abweichungen auf Baseneb
- Seite 79 und 80: Y13, Y57 Y18, Y65 Y23 Y153 Y159 Y16
- Seite 81 und 82: - 81 - Verifikation der Protein-Int
- Seite 83 und 84: - 83 - Resultate der GST-Pulldown-E
- Seite 85 und 86: - 85 - λ-Phagen-PCR-Screen Um die
- Seite 87: Pvu I (2416) Ampicillin Pvu I (4438
- Seite 91 und 92: - 91 - Verdaus von 5441 bp in zwei
- Seite 93 und 94: - 93 - Morula-Aggregation von ES-Ze
- Seite 95 und 96: - 95 - 2. Virtueller Northern für
- Seite 97 und 98: ISH - 97 - Abbildung 73: Die Abbild
- Seite 99 und 100: Abbildung 75: In der rechten Abbild
- Seite 101 und 102: cv ia da Abbildung 78: In diesem ho
- Seite 103 und 104: - 103 - Abbildung 82: E12ct Embryo
- Seite 105 und 106: ca na ok ct lca lca lca ct ct co ct
- Seite 107 und 108: le Il caa ia pe Il ila ao caa cav i
- Seite 109 und 110: 3 4 5 6 ia 7 8 9 10 11 12 13 1 2 ao
- Seite 111 und 112: tt Il ma de - 111 - Abbildung 94: I
- Seite 113 und 114: - 113 - TRIM46 im Whole-Mount-Gehir
- Seite 115 und 116: Abbildung 101: Adultes Gehirn von T
- Seite 117 und 118: Cgl Cgl TN GCl HI AMY AMY Pir Abbil
- Seite 119 und 120: - 119 - Genaue Lokalisation der TRI
- Seite 121 und 122: - 121 - Zur weiteren Spezifizierung
- Seite 123 und 124: Auge Magen, Duodenum, Pankreas, Dar
- Seite 125 und 126: Niere - 125 - Abbildung 119: (A) Qu
- Seite 127 und 128: Harnblase TRIM46-lacZ gl Prox1 gl T
- Seite 129 und 130: pa Br Abbildung 127: lacZ-Färbung
- Seite 131 und 132: - 131 - lacZ-Färbung in Tumorgeweb
- Seite 133 und 134: Diskussion - 133 - Microarray-Analy
- Seite 135 und 136: - 135 - Publikationen sich damit be
- Seite 137 und 138: - 137 - Klon 103 - Etv5 Das Gen Etv
Acc 65I (26)<br />
SmaI (22)<br />
ApaI (18)<br />
KpnI (12)<br />
Acc65I (8)<br />
BamHI (73)<br />
Sa cII (48)<br />
XbaI (32)<br />
Ligation:<br />
- 89 -<br />
5’…ATGGCTGAGGGTGAGGATATGCAGACCTTCACTTCCATCATGGATGCACTAGGTACCTCTAGAATGCA<br />
TTCCGCGGGTTTTCATGTACCCAGCATGGGGGATCCCGTCGTTTTA…3’<br />
Fortlaufendes Leseraster:<br />
5’…ATG.GCT.GAG.GGT.GAG.GAT.ATG.CAG.ACC.TTC.ACT.TCC.ATC.ATG.GAT.GCA.CTA.<br />
GGT.ACC.TCT.AGA.ATG.CAT.TCC.GCG.GGT.TTT.CAT.GTA.CCC.AGC.ATG.GGG.GAT.CCC<br />
.GTC.GTT.TTA…3’<br />
Hinzufügen der 3’-Flanke <strong>und</strong> Rekonstitution <strong>von</strong> Neomycin:<br />
KpnI (30)<br />
XbaI (32)<br />
Sa cII (48)<br />
lacZ-pA<br />
EcoR V (118 0)<br />
Thymidine-Kinase<br />
Bam HI (15257)<br />
5'-Flanke<br />
Acc 65I (14135)<br />
Acc 65I (13073)<br />
Xba I (13067)<br />
BamHI (73)<br />
Xho I (17318)<br />
SalI (17312)<br />
Eco RV (16688)<br />
EcoRV (16584)<br />
SacII (13057)<br />
Bam HI (13026)<br />
EcoRV (1180)<br />
lacZ-pA<br />
pGK-Neomycin-pA<br />
EcoRI (3071)<br />
pKC414-lacZ-Neo<br />
5207 bp<br />
pGK-Neomycin-pA<br />
BamH I (3527)<br />
pKC414-lacZ-Neo + 3'-Flanke<br />
1246 0 bp<br />
XbaI (4877)<br />
Sp e I (3792) Sp eI (5169)<br />
3'-Flanke<br />
Not I geschnitten + Spe I partiell verdaut<br />
alternativ ginge nur Spe I<br />
Eco RV (11923)<br />
Spe I (3792)<br />
BamHI (3527)<br />
Acc 65I (17333)<br />
SacII (664)<br />
XbaI (4877)<br />
XhoI (5163)<br />
Hind III (804 5)<br />
Sa lI (6239 )<br />
pBS II-KS + TK + 5'-Flanke<br />
+ lacZ-Neo + 3'-Flanke<br />
lacZ-pA<br />
Ampicillin<br />
ATG<br />
ORF<br />
Bam HI (9572)<br />
Eco RV (9566)<br />
19539 bp<br />
Not I (670)<br />
SpeI (9307)<br />
SpeI (677)<br />
Bam HI (683)<br />
Spe I (12422)<br />
BamHI (12416)<br />
Xba I (8222)<br />
Acc 65I (3235)<br />
Xho I (7936)<br />
pGK-Neomycin-pA<br />
Acc 65I (3661)<br />
SalI (6860)<br />
Xho I (5163)<br />
3'-Flanke<br />
Acc 65I (4726)<br />
Acc 65I (5470)<br />
XhoI (5175)<br />
Not I (5182)<br />
XbaI (12428)<br />
NotI (12435)<br />
Xho I (7942)<br />
Not I + Spe I<br />
oder nur Spe I<br />
Ampicillin<br />
Afl III (8355)<br />
SalI (6866)<br />
Acc 65I (9788)<br />
Xho I (9773)<br />
Thymidine-Kinase<br />
Eco RI (7718)<br />
Bam HI (7712)<br />
Pvu I (9618)<br />
Ampicillin<br />
Pvu I (500)<br />
pBS II-KS + 3'-Flanke<br />
10163 bp<br />
Not I (670)<br />
SpeI (683)<br />
pBS II-KS + TK + 5'-Flanke<br />
+ lacZ-Neo.trunc<br />
5'-Flanke<br />
Acc 65I (6590)<br />
Not I (670)<br />
11994 bp<br />
ATG<br />
ORF<br />
Xba I (677)<br />
Xba I (5522)<br />
Bam HI (689)<br />
3'-Flanke<br />
Acc 65I (5528)<br />
Fertiger KO-Konstruktvektor, der <strong>für</strong> <strong>die</strong><br />
homologe Rekombination in ES-Zellen mit Not I<br />
linearisiert wurde.<br />
Pvu I (886)<br />
Afl III (2737)<br />
pGK-Neomycin-truncated<br />
Bam HI (5481)<br />
Spe I (1762)<br />
Bam HI (2027)<br />
Eco RI (2483)<br />
lacZ-pA